-
刨花润楠(Machilus pauhoi Kanehira.)又名刨花楠,是樟科(Lauraceae)润楠属(Machilus)亚热带常绿乔木,常散生在海拔800 m以下的山坡灌丛或山沟疏林,幼龄期喜阴耐湿生长较缓慢,中龄期喜光喜湿生长迅速[1-3]。刨花润楠天然分布于我国的广东、广西、福建、江西、湖南、浙江和安徽等省(区),生长十分迅速并具有极强的萌蘖更新能力,采伐后通过伐桩萌蘖更新的林分生长速度更快,是我国南方地区重点发展的优良高产乡土树种之一[4-5]。刨花润楠应用范围十分广泛,是优质珍贵的用材树种,木材被广泛应用于家具制作和建筑装饰等领域;其新出嫩叶呈粉红色或红棕色,加之树形美观,亦可作为优美的庭院绿化与观赏树种应用;其木材、树皮富含胶质,树叶可提取精油,是上好薰香制品的主要工业原料;同时具有良好的防风固土和防火特性[2-3, 6-8]。总体而言,刨花润楠是经济价值与生态价值均较高的优良树种。目前,刨花润楠野生种质资源正受到日益严重的破坏,利用分子标记技术研究其遗传多样性,对该树种的保护和育种策略的制定等具有重要的理论和实践意义。
简单重复序列(SSR),又称之为微卫星,近年来,随着SSR分子标记技术的日趋成熟,因其具有共显性、操作简便、稳定可靠、重复性好、多态性丰富以及近缘属间具有一定的通用性等优点,已广泛应用于生物遗传多样性、基因定位、资源亲缘关系、品种鉴定和遗传图谱构建等方面[9-14]。
SSR是基于PCR技术的一种分子标记技术,其扩增结果易受反应体系中各因素的影响[15],稳定的PCR反应体系是进行SSR分析的前提。因此,本试验旨在利用单因素结合正交设计试验,对影响刨花润楠SSR-PCR反应体系的各因素进行逐步优化,建立稳定的反应体系。并借鉴樟科植物文献报道的SSR引物,筛选多态性高、稳定性和重复性好且适用于刨花润楠的引物,分析刨花润楠的遗传多样性特点、遗传结构与划分遗传类群,为制定保护和育种策略提供重要依据。
-
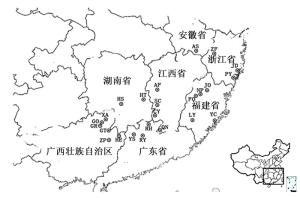
从全国7省(区)24个刨花润楠天然林分中,选择生长良好、无病虫害的母树分单株采集成熟果实。母树间相距100 m以上,选择16株,数量不足者按实际单株量全部采集。经洗去果皮后,沙藏促其萌发,种植于广州市华南农业大学教学科研基地。次年,采集子代苗嫩叶用于DNA提取。种源信息见表 1和图 1。
表 1 刨花润楠种源信息表
Table 1. Information sheets about different provenances of Machilus pauhoi
省份
Province种源名称、代码及样本量
Provence Code and Sample capacity广西 兴安
XA (16)贺州
HE (12)昭平
ZP (13)灵川
GO (15)恭城
GT (11)阳朔
GR (8)福建 建瓯
JO (15)顺昌
NP (15)永春
YC (15)龙岩
LY (4)将乐
FO (6)江西 遂川
SC (15)安福
AF (16)全南
QN (11)崇义
CY (6)广东 仁化
RH (14)阳山
YS (14)乳源
RY (9)浙江 建德
ZF (14)温州
JD (15)平阳
PY (16)湖南 茶陵
HT (13)祁阳
HS (11)安徽 祁门
AS (4) -
本研究所用SSR引物来源于樟科润楠属植物红楠(Machilus thunbergii Sieb. et Zucc.)和Machilus pseudokobu及鳄梨属植物鳄梨(Persea americana Mill)3个物种公开发布的187对SSR引物[16-21],由深圳华大公司合成。详细信息参见表 2。
表 2 SSR引物来源及信息
Table 2. The source and information of SSR primer in M.pauhoi
-
以展叶15 d左右的新鲜叶片为材料,采用EZNAⓇ high-performance DNA mini Kit试剂盒提取基因组DNA。使用0.8%琼脂糖凝胶电泳和超微量紫外分光光度计(Thermo NanoDrop1000)对提取的DNA进行质量、纯度和浓度检测。检测后,将浓度稀释至50 ng·μL -1,置于-20℃下保存备用。
-
采用L16(45)正交试验设计(表 3),对模板DNA、Taq酶、Mg2+、dNTPs和引物进行5因素4水平筛选分析。反应体系总体积为20 μL,均含有2 μL 10×Buffer (Mg2+ free),根据实际情况,再补加重蒸水至20 μL。最后,以产物扩增条带清晰度,非特异扩增为标准,效果最好的记16,最差的记为1,对该组合评分数据用SPSS20.0进行方差分析[22-23]。
表 3 SSR-PCR反应的L16(45)正交试验设计
Table 3. L16(45)orthogonal design of SSR-PCR reaction
编号
No.Taq酶
Taq DNA polymerase/(U)Mg2+/(mmol·L-1) dNTPs/(mmol·L-1) 引物
Primer/(μmol·L-1)DNA/(ng) 1 0.75(1) 1.87 5(1) 0.187 5(1) 0.125(1) 20(1) 2 0.75 2.50 0(2) 0.250 0(2) 0.250(2) 30(2) 3 0.75 3.12 5(3) 0.312 5(3) 0.375(3) 40(3) 4 0.75 3.75 0(4) 0.375 0(4) 0.500(4) 50(4) 5 1.00(2) 1.875 0.250 0 0.375 50 6 1.00 2.500 0.187 5 0.500 40 7 1.00 3.125 0.375 0 0.125 30 8 1.00 3.750 0.312 5 0.250 20 9 1.25(3) 1.875 0.312 5 0.500 30 10 1.25 2.500 0.375 0 0.375 20 11 1.25 3.125 0.187 5 0.250 50 12 1.25 3.750 0.250 0 0.125 40 13 1.50(4) 1.875 0.375 0 0.250 40 14 1.50 2.500 0.312 5 0.125 50 15 1.50 3.125 0.250 0 0.500 20 16 1.50 3.750 1.187 5 0.375 30 -
反应程序为:94℃变性9 min; 30个循环(94℃0.5 min,57℃0.5 min,72℃0.5 min);72℃延伸5 min;4℃保存。PCR产物用2%的琼脂糖凝胶电泳,并用凝胶电泳成像分析系统(美国伯乐)成像保存。
-
用不同种源DNA和引物及其所对应的最适退火温度检验最佳体系, 最佳体系确定后进行引物筛选。先选用4个种源DNA进行初筛,再选用8个种源DNA进行复筛,扩增产物用2%的琼脂糖凝胶电泳进行检测,确定为有效引物后,扩增产物用6%变性聚丙烯酰胺凝胶银染染色检测。
-
确定有效的引物由上海生工生物工程公司完成PCR产物的毛细管电泳检测和数据收集工作。利用Convert1.31软件将SSR谱带统计结果进行数据多样格式转换。利用POPGENE1.32软件计算各群体观测等位标记数(Na)、观察杂合度(Ho)和期望杂合度(He);利用PowerMarker v3.25软件计算每个SSR位点的多态性信息量(PIC);用FSTAT软件计算遗传分化系数(Gst),基因流Nm=Gst/4×(1-Gst);利用GenAlex6.5检测位点哈迪-温伯格平衡(HWE);利用Structure2.3软件进行群体遗传结构分析;采用POPTREE软件进行UPGMA法聚类分析。
-
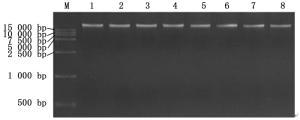
用超微量紫外分光光度计检测提取的DNA,OD260/OD280比值均在1.7~1.9之间,OD260/ OD230比值均在1.8~3.0之间,说明所提取的DNA纯度较高。使用0.8%琼脂糖凝胶电泳结果(图 2)表明:DNA均呈现一条清晰完整的主带,无拖尾和降解,无明显的RNA存在。因此,所提DNA可以适用于后续SSR分析。
-
从正交试验产物电泳结果(图 3)可以看出:处理5、7、8和9的条带较清晰,结合经济成本等因素,最终确定处理5为最佳体系,各因素对应浓度分别为:Taq酶1.0 U,dNTPs 0.25 mmol·L-1,Mg2+1.25 mmol·L-1,引物0.5 μmol·L-1,DNA 50 ng。
应用SPSS20.0软件对这16个组合的评分数据进行方差分析,结果(表 4)表明:除引物外,Taq酶、dNTPs、Mg2+和模板DNA对试验结果影响均达到极显著水平。依据F值大小判断各因素对刨花润楠SSR-PCR反应体系的影响程度依次为:Taq酶> dNTPs>Mg2+>DNA>引物。
表 4 正交设计方差分析表
Table 4. Variance analysis of orthogonal design
变异来源
Source平方和SS 自由度
DF均方
MSF-Value 校正模型 674.000 15 44.933 119.822** Taq酶 400.500 3 133.500 356.000** Mg2+ 92.000 3 30.667 81.778** dNTPs 171.000 3 57.000 152.000** 引物 1.500 3 0.500 1.333 DNA 9.000 3 3.000 8.000** 误差 6.000 16 0.375 总计 2 992.000 32 校正后误差 680.000 31 注:“**”表示P≤0.01差异极显著。
Notes: Symbol “**” means the variation was significantly different. -
用部分引物及其对应退火温度对最佳体系进行验证,图 4A、4B为琼脂糖凝胶电泳图,适用于引物初筛。可以看出,该体系稳定可靠,条带清晰,多态性高,非特异性条带少,适用于后续引物筛选。

图 4 部分引物在最佳反应体系下的扩增结果
Figure 4. Amplication results of some primers in the optimal SSR-PCR reaction system
图 4C、4D为通过银染染色的6%变性聚丙烯酰胺凝胶电泳图。因变性聚丙烯酰胺凝胶电泳可将相差一至数个碱基的DNA链分开,分辨率高,因此,适用于对初筛引物的进一步复筛,通常会把复筛后的引物作为最终筛选引物。其中,图 4C为3对引物Mt59、Mt60和Mt61分别在8个种源(HT、YC、AF、ZF、RH、AS、QN和XA)DNA样本中的扩增条带图,图 4D为引物Mt146分别在2个种源(RH和XA)各15个家系DNA样本中的扩增条带图。由此可见,上述引物不仅能检测出不同种源间的差异,也能检测出种源内不同家系的差异,因此,可作为最终筛选引物。最终,从187对候选SSR引物中共筛选到具有多态性高的引物12对(表 5),可用于后续刨花润楠种群遗传多样性分析。
表 5 筛选到的12对SSR引物序列
Table 5. SSR primer sequences of 12 SSR primers in M.pauhoi
代码
Code正向引物序列(5’-3’)
Forward primer sequence(5’-3’)反向引物序列(5’-3’)
Reverse primer sequence(5’-3’)Mt59 F:ACCCAATCAACAAACAAACCC R:CGTTTCCCCAATCCATTTCT Mt60 F:CGAAGAAGGATAGTCTGAAAACCC R:GAGGAAGGATCGGAAGAGAGG Mt61 F:AACCCTAACGGATTTCAACTAC R:ACGGTATAGCTCCTTCCATTC Mt67 F:ACACCCAACAGATGTGGATAGATAAG R:CAGATGAAAAGAACATGGCATTGA Mt90 F:GCAAGGCATTACGATGTCA R:CTCTAGTGGACAAAATCGACAA Mt131 F:CAGAGAATACGGATCTTTGC R:GTTCGAAGAAGCCTCAGTTA Mt139 F:TTACCAGTGCTCCTGCTAAT R:TGCTCTCAAACCACTTCTCT Mt145 F:CCCTTTCCAAGTTTCCTAAC R:GTGCAGAGGTAAGTCACCAT Mt146 F:AGCATGAGAGCAGAATCAAG R:ATCCCAACAGAAGCAGTTTA Mt153 F:CCTCAGGTTGAGACCTACTG R:CGGTGGCCACTATTAACC Mt154 F:CTCTTCTTTTGCTTTGTTCG R:CGTTACGTTAACTGCATCTC Mt169 F:ATTGCTGCATTTTCTTGTTT R:AGGGATTAGTCCAACCATTT -
12对SSR引物在24个刨花润楠种源中均有多态性扩增(表 6),共检测到181个等位标记,观测等位标记数(Na)、观测杂合度(Ho)和期望杂合度(He)平均值分别为15.083、0.576和0.751。等位标记数(Na)是描述共显性SSR标记遗传多样性的最适参数,刨花润楠平均等位标记数Na=15.083,表明刨花润楠群体遗传多样性处于较高水平。多态性信息PIC介于0.575~0.861之间,表明筛选到的12对引物多态性较高。经检测,这12对引物均未偏离哈迪-温伯格平衡,各引物间相互独立,不存在连锁不平衡,适用于后续遗传多样性研究。
表 6 12对SSR引物遗传多样性参数
Table 6. Genetic diversity parameters of 12 SSR primers in M.pauhoi
代码
Code观测等位标记数
Na观测杂合度
Ho期望杂合度
He多态性信息量
PIC哈迪-温伯格平衡检测
Hardy-Weinberg equilibrium(HWE)基因流
NmMt59 12 0.635 0.715 0.683 ns 2.165 Mt60 13 0.544 0.798 0.773 ns 0.604 Mt61 13 0.476 0.604 0.575 ns 1.337 Mt67 12 0.361 0.742 0.703 ns 1.073 Mt90 7 0.519 0.672 0.611 ns 1.169 Mt131 11 0.542 0.696 0.660 ns 1.445 Mt139 28 0.463 0.803 0.787 ns 1.591 Mt145 23 0.790 0.835 0.816 ns 3.156 Mt146 16 0.913 0.875 0.861 ns 2.177 Mt153 11 0.406 0.642 0.594 ns 0.840 Mt154 15 0.712 0.874 0.859 ns 1.725 Mt169 20 0.552 0.757 0.742 ns 0.724 均值
Mean15.083 0.576 0.751 0.722 ns 1.500 注:ns表示没有显著偏离哈迪-温伯格平衡。
Note:Symbol “ns” means no significant deviations from Hardy-Weinberg equilibrium.基因流(Nm)是植物种群间的基因流动形成的,种子植物群体间的最主要基因流是通过种子或花粉传播而产生[24-25]。当基因流>1时,说明种群间存在着频繁的基因交流,防止因遗传漂变引起的居群遗传分化,有利于保持群体的遗传稳定性[26]。刨花润楠群体间的基因流平均值为1.500,表明刨花润楠群体间存在频繁的基因交流。
-
基于模型STRUCTURE运算结果分析刨花润楠遗传结构,24个种源被分为3组,或称为3个基因池(图 5)。第Ⅰ类主导基因池颜色绿色,包括福建3个种源JO、NP和FO;第Ⅱ类主导基因池颜色为蓝色,包括广西、福建和江西三省(区)8个种源,分别为:广西GO、GT、GR和XA 4个种源,福建YC和LY 2个种源,江西CY和QN 2个种源;第Ⅲ类主导基因池颜色为红色,包括除福建省外的其它6个省(区)13个种源,覆盖范围最广,种源数量最多。
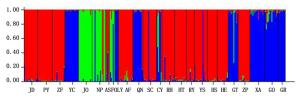
图 5 利用STRUCTURE获得的刨花润楠遗传结构图
Figure 5. Structure analysis of 24 provenances in M.pauhoi by STRUCTURE software
依据Nei’s遗传距离对24个刨花润楠种源进行聚类分析(图 6),该聚类结果同STRUCTURE软件分析结果一致性较好,同样把24个种源分为3组。第一组包括福建种源JO、NP和FO(100/100),对应STRUCTURE分析中绿色基因池;第二组包括福建YC、LY,广西GO、GR、GT、XA,江西CY和QN 8个种源(75/100),对应STRUCTURE分析中蓝色基因池;第三组包括江西SC、AF,广西ZP、HE,湖南HT、HS,广东RH、YS、RY,浙江ZF、JD、PY和安徽AS 13个种源(55/100),对应STRUCTURE分析中红色基因池。
-
SSR-PCR体系是一个受多因子影响的复杂体系,各因子间常存在交互作用,且不同物种的最佳反应条件也不尽相同[27]。因此,优化建立试验树种的SSR-PCR最佳体系是进行后续遗传研究的前提。
前人研究成果表明,不同树种PCR反应体系中各因素对体系的影响程度也不尽相同。如红椿SSR-PCR体系中Mg2+ 影响程度最大[22],引物浓度则是桉树SSR-PCR体系最重要的影响因素[23]。本研究的方差分析结果表明,Taq酶、dNTPs、Mg2+和DNA对试验结果影响均达到极显著水平,各因素对SSR-PCR体系的影响程度依次为:Taq酶>dNTPs>Mg2+>DNA>引物, 其中, Taq酶是最重要的影响因素。Taq酶是一种Mg2+依赖性酶,浓度过低,反应灵敏度变差,扩增条带较少;浓度过高,则反应特异性降低,条带弥散。因此,在刨花润楠SSR-PCR体系优化时应特别注意Taq酶的用量。
目前,SSR体系的优化普遍采用正交设计的方法[28-29]。本试验结果表明,按照此方法确立与优化的刨花润楠SSR-PCR最佳体系,可以得到较好的扩增结果,并能验证不同种源间和种源内不同家系的差异[30],可以用于后续遗传多样性研究。
常用PIC值来衡量不同位点多态性高低的程度,揭示引物贡献率的高低。一般认为,PIC>0.5时,引物贡献率较高,多态性较好,选取的引物可以最大程度的反映遗传多样性;当0.25 < PIC < 0.5或PIC < 0.25时,则说明多态位点处于中等或较低水平,引物贡献率中等或较低[31-32]。本研究中PIC范围为0.575~0.861,平均值为0.722,表明筛选到的12对SSR引物多态性较高,能有效揭示刨花润楠不同种源的遗传多样性水平。
刨花润楠遗传多样性较高,群体间存在频繁的基因交流,这可能与其地理分布、生活习性和繁育系统密切相关。刨花润楠广泛分布于我国热带和亚热带地区的多个省份,花期较集中,依靠风力授粉扩大了其花粉传播范围。在野外调查中发现,天然条件下,刨花润楠喜湿耐阴,多生长在溪流旁,而武夷山脉和雪峰山之间存在许多南北流向的溪流,不排除水力传播在刨花润楠种子扩散中也起到一定作用。除此之外,类似于闽楠(Phoebe boumei (Hemsl.) Yang)、舟山新木姜子(Neolitsea sericea (Bl.) Koidz.)和樟桂属等树种,鸟类或其它动物活动也可能一定程度上扩大了刨花润楠种子扩散范围[33-36]。刨花润楠作为香薰制品、润发剂和粘合剂等用途而频繁流通于人类活动中,或许也是刨花润楠种子扩散的一个途径。因此,南岭及南岭以北的大部分种源虽然地理距离跨越较大但仍聚为一类。
聚类分析中还发现,福建种源LY、YC跨越武夷山脉与江西种源CY、QN及雪峰山东侧的广西种源XA、GT、GO、GR聚为一类,其中,南岭东面4个种源(LY、YC、CY、QN)聚为1个亚类,南岭西面4个种源(XA、GT、GO、GR)聚为另1个亚类。分析可能原因:刨花润楠起源时间早于后期形成的喜马拉雅山和横断山脉,山体运动及第四纪冰川的出现,加大了刨花润楠种群间的遗传分化,最终构成了现有的种群遗传结构。分布在武夷山脉附近的LY、YC、CY和QN种源,因武夷山脉形成的山体屏障,从西向东花粉及种子扩散方式较弱[37],从而保留了与可能的冰期避难所XA、GT、GO和GR种源较近的遗传关系[30]。
目前,仅少量刨花润楠天然分布区建立了自然保护区,大多数刨花润楠仍处于过度采伐的状态,随着刨花润楠资源的开发利用,刨花润楠野生资源数量在急剧减少。因此,在原有生境进行保护的同时,加强异地保存,根据现有的种群遗传结构及划分的遗传类群,收集种质资源并建立刨花润楠基因库。加强人工繁育技术,最大限度的保护刨花润楠遗传多样性,尤其关注可能的冰期避难所广西种源以及天然种群数量较少的福建种源。
-
本研究利用樟科植物SSR引物对刨花润楠进行SSR-PCR体系优化和分析,建立了最佳体系,分析结果表明,刨花润楠遗传多样性较高,群体间存在频繁的基因交流,24个种源可分为3大类。依据刨花润楠天然种群遗传结构,原地保护结合异地保存,收集并建立刨花润楠基因库,可为该种质资源的保护及育种策略的制定提供重要依据。
刨花润楠SSR-PCR体系优化及天然种群遗传多样性研究
Optimization of SSR-PCR Reaction System and Study on Genetic Diversity of Natural Populations of Machilus pauhoi
-
摘要:
目的 建立刨花润楠SSR-PCR最佳反应体系,从樟科树种SSR引物中筛选多态性高的引物,并对刨花润楠遗传多样性进行分析。 方法 对影响PCR反应体系的5个因素设置7个水平,利用正交设计L16(45)进行优化,确定最佳体系,并用该体系从187对候选引物中进行引物筛选。利用软件POPGENE1.32、PowerMarkerv3.25、FSTAT、GenAlex6.5、Structure2.3和POPTREE分别计算观测等位基因数目(Na)、观察杂合度(Ho)、期望杂合度(He)、多态性信息量(PIC)、基因流(Nm),进行群体遗传结构分析和UPGMA法聚类分析。 结果 刨花润楠最佳体系(20 μL)为:Taq酶1.0 U、dNTPs 0.25 mmol·L-1、Mg2+ 1.25 mmol·L-1、引物0.5 μmol·L-1、模板50 ng。最终筛选出12对具有多态性高的SSR引物。Na、Ho、He和PIC的平均值分别为15.083、0.576、0.751和0.722,表明种群具有较丰富的遗传多样性;Nm平均值为1.500,种群间存在频繁的基因交流;UPGMA将24个种源聚为3类,与Structure分析结果一致。 结论 本研究成功优化了刨花润楠SSR-PCR反应体系,并获得12对适用于刨花润楠的SSR引物,刨花润楠种群遗传多样性丰富,种群间存在频繁的基因交流,24个种源可聚为3类。 Abstract:Object To establish SSR-PCR reaction system of Machilus pauhoi, screen the high polymorphic primers from the SSR primers of Lauraceae, and to investigate the genetic diversity of M. pauhoi. Method In order to establish the optimum SSR-PCR reaction system of M. pauhoi, seven concentration levels were set for each of five factors to determine the suitable concentration range by using L16(45) orthogonal design. The system was used to filter primers from 187 candidate primers. The software of POPGENE1.32, PowerMarkerv3.25, FSTAT, GenAlex6.5, Structure2.3 and POPTREE were used to calculate the observed allelic number (Na), observed heterozygosity (Ho), expected heterozygosity (He), Polymorphism Information Content (PIC), gene flow (Nm), the genetic structure and cluster analysis based on the unweighted pair group method of arithmetic averages (UPGMA). Result The optimal reaction system was established, the optimum concentration of five factors are as follows:Taq polymerase, dNTPs, Mg2+, primers and template DNA were 1.0 U·μL-1, 0.25 mmol·L-1, 1.25 mmol·L-1, 0.5 μmol·L-1and 50 ng in a total volume of 20 μL, respectively. Twelve pairs of SSR primers with high polymorphism were screened. The average Na, Ho, He and PIC were 15.083, 0.576, 0.751, and 0.722, respectively, which means higher genetic diversity in M. pauhoi. The average Nm was 1.500, which means high gene flow existed among the provenances. The analysis with UPGMA was consistent with Structure software which indicated that the twenty-four provenances could be divided into three groups. Conclusion The study optimizes the SSR-PCR reaction system successfully, twelve primers are screened out from 187 candidate primers using the optimal reaction system.There is higher genetic diversity in M. pauhoi population. The limited gene flow exists in these provenances, and the twenty-four provenances can be divided into three groups. -
Key words:
- Machilus pauhoi
- / SSR-PCR
- / system optimization
- / populations
- / genetic diversity
-
表 1 刨花润楠种源信息表
Table 1. Information sheets about different provenances of Machilus pauhoi
省份
Province种源名称、代码及样本量
Provence Code and Sample capacity广西 兴安
XA (16)贺州
HE (12)昭平
ZP (13)灵川
GO (15)恭城
GT (11)阳朔
GR (8)福建 建瓯
JO (15)顺昌
NP (15)永春
YC (15)龙岩
LY (4)将乐
FO (6)江西 遂川
SC (15)安福
AF (16)全南
QN (11)崇义
CY (6)广东 仁化
RH (14)阳山
YS (14)乳源
RY (9)浙江 建德
ZF (14)温州
JD (15)平阳
PY (16)湖南 茶陵
HT (13)祁阳
HS (11)安徽 祁门
AS (4)表 2 SSR引物来源及信息
Table 2. The source and information of SSR primer in M.pauhoi
表 3 SSR-PCR反应的L16(45)正交试验设计
Table 3. L16(45)orthogonal design of SSR-PCR reaction
编号
No.Taq酶
Taq DNA polymerase/(U)Mg2+/(mmol·L-1) dNTPs/(mmol·L-1) 引物
Primer/(μmol·L-1)DNA/(ng) 1 0.75(1) 1.87 5(1) 0.187 5(1) 0.125(1) 20(1) 2 0.75 2.50 0(2) 0.250 0(2) 0.250(2) 30(2) 3 0.75 3.12 5(3) 0.312 5(3) 0.375(3) 40(3) 4 0.75 3.75 0(4) 0.375 0(4) 0.500(4) 50(4) 5 1.00(2) 1.875 0.250 0 0.375 50 6 1.00 2.500 0.187 5 0.500 40 7 1.00 3.125 0.375 0 0.125 30 8 1.00 3.750 0.312 5 0.250 20 9 1.25(3) 1.875 0.312 5 0.500 30 10 1.25 2.500 0.375 0 0.375 20 11 1.25 3.125 0.187 5 0.250 50 12 1.25 3.750 0.250 0 0.125 40 13 1.50(4) 1.875 0.375 0 0.250 40 14 1.50 2.500 0.312 5 0.125 50 15 1.50 3.125 0.250 0 0.500 20 16 1.50 3.750 1.187 5 0.375 30 表 4 正交设计方差分析表
Table 4. Variance analysis of orthogonal design
变异来源
Source平方和SS 自由度
DF均方
MSF-Value 校正模型 674.000 15 44.933 119.822** Taq酶 400.500 3 133.500 356.000** Mg2+ 92.000 3 30.667 81.778** dNTPs 171.000 3 57.000 152.000** 引物 1.500 3 0.500 1.333 DNA 9.000 3 3.000 8.000** 误差 6.000 16 0.375 总计 2 992.000 32 校正后误差 680.000 31 注:“**”表示P≤0.01差异极显著。
Notes: Symbol “**” means the variation was significantly different.表 5 筛选到的12对SSR引物序列
Table 5. SSR primer sequences of 12 SSR primers in M.pauhoi
代码
Code正向引物序列(5’-3’)
Forward primer sequence(5’-3’)反向引物序列(5’-3’)
Reverse primer sequence(5’-3’)Mt59 F:ACCCAATCAACAAACAAACCC R:CGTTTCCCCAATCCATTTCT Mt60 F:CGAAGAAGGATAGTCTGAAAACCC R:GAGGAAGGATCGGAAGAGAGG Mt61 F:AACCCTAACGGATTTCAACTAC R:ACGGTATAGCTCCTTCCATTC Mt67 F:ACACCCAACAGATGTGGATAGATAAG R:CAGATGAAAAGAACATGGCATTGA Mt90 F:GCAAGGCATTACGATGTCA R:CTCTAGTGGACAAAATCGACAA Mt131 F:CAGAGAATACGGATCTTTGC R:GTTCGAAGAAGCCTCAGTTA Mt139 F:TTACCAGTGCTCCTGCTAAT R:TGCTCTCAAACCACTTCTCT Mt145 F:CCCTTTCCAAGTTTCCTAAC R:GTGCAGAGGTAAGTCACCAT Mt146 F:AGCATGAGAGCAGAATCAAG R:ATCCCAACAGAAGCAGTTTA Mt153 F:CCTCAGGTTGAGACCTACTG R:CGGTGGCCACTATTAACC Mt154 F:CTCTTCTTTTGCTTTGTTCG R:CGTTACGTTAACTGCATCTC Mt169 F:ATTGCTGCATTTTCTTGTTT R:AGGGATTAGTCCAACCATTT 表 6 12对SSR引物遗传多样性参数
Table 6. Genetic diversity parameters of 12 SSR primers in M.pauhoi
代码
Code观测等位标记数
Na观测杂合度
Ho期望杂合度
He多态性信息量
PIC哈迪-温伯格平衡检测
Hardy-Weinberg equilibrium(HWE)基因流
NmMt59 12 0.635 0.715 0.683 ns 2.165 Mt60 13 0.544 0.798 0.773 ns 0.604 Mt61 13 0.476 0.604 0.575 ns 1.337 Mt67 12 0.361 0.742 0.703 ns 1.073 Mt90 7 0.519 0.672 0.611 ns 1.169 Mt131 11 0.542 0.696 0.660 ns 1.445 Mt139 28 0.463 0.803 0.787 ns 1.591 Mt145 23 0.790 0.835 0.816 ns 3.156 Mt146 16 0.913 0.875 0.861 ns 2.177 Mt153 11 0.406 0.642 0.594 ns 0.840 Mt154 15 0.712 0.874 0.859 ns 1.725 Mt169 20 0.552 0.757 0.742 ns 0.724 均值
Mean15.083 0.576 0.751 0.722 ns 1.500 注:ns表示没有显著偏离哈迪-温伯格平衡。
Note:Symbol “ns” means no significant deviations from Hardy-Weinberg equilibrium. -
[1] 赵红梅, 肖志豪, 李勇.刨花楠的扦插繁殖[J].江西林业科技, 2005(4):8-10. doi: 10.3969/j.issn.1006-2505.2005.04.004 [2] 吴国训, 吴田兵, 查宝源, 等.低温胁迫对刨花楠苗期细胞保护系统及生理生化物质的影响[J].江西林业科技, 2008(4):14-16. doi: 10.3969/j.issn.1006-2505.2008.04.004 [3] 陈国彪.刨花楠的利用与培育技术[J].广西林业科学, 2004, 33(4):212-213. doi: 10.3969/j.issn.1006-1126.2004.04.014 [4] 张敏, 蓝芳菊, 谌礼兵.桂北地区刨花润楠发展前景及栽培技术[J].南方农业, 2013, 7(12):74-77. doi: 10.3969/j.issn.1673-890X.2013.12.020 [5] 朱宏光, 杨柳, 温远光, 等.广西大明山刨花润楠种群结构及其分布格局研究[J].广东农业科学, 2015, 42(12):147-151. doi: 10.3969/j.issn.1004-874X.2015.12.029 [6] 钟全林, 胡滨, 程建华, 等.粉用刨花楠工业原料林栽培技术研究[J].江西农业大学学报, 2008, 30(2):257-262. doi: 10.3969/j.issn.1000-2286.2008.02.015 [7] 郭晓敏, 牛德奎, 孙科辉.优良阔叶树种——刨花楠木材构造性质及用途的研究[J].江西农业大学学报, 1999, 21(3):391-394. [8] 冯建民, 何贵平, 骆文坚, 等.刨花楠开花结实习性及其种子贮藏试验初报[J].浙江林业科技, 2005, 25(3):23-25. doi: 10.3969/j.issn.1001-3776.2005.03.006 [9] 李红英, 李康琴, 胥猛, 等。北美鹅掌楸EST-SSR跨属间通用性[J].东北林业大学学报, 2011, 39(2):28-30. doi: 10.3969/j.issn.1000-5382.2011.02.009 [10] 邓绍勇, 温强, 李康琴, 等.大青属植物通用性SSR引物筛选及应用[J].中草药, 2014, 45(22):3317-3322. doi: 10.7501/j.issn.0253-2670.2014.22.019 [11] Varshney R K, Graner A, Sorrells M E. Genic microsatellite marker in plants:features and applications[J].Trends in Biotechnology, 2005, 23(1):48-55. [12] Sharma R K, Gupta P, Sharma V, et al. Evaluation of rice and sugarcane SSR markers for phylogenetic and genetic diversity analyses in bamboo[J].Genome, 2008, 51:91-103. doi: 10.1139/G07-101 [13] Zhebentyayeva T, Reighard G, Gorina V. et al. Simple Sequence Repeat (SSR) analysis for assessment of genetic variability in apricot germplasm[J].Theoretical and Applied Genetics, 2003, 106(3):435-444. doi: 10.1007/s00122-002-1069-z [14] Hormaza J. I. Molecular characterization and similarity relationships among apricot (Prunus armeniaca L.) genotypes using simple sequence repeats[J]. Theor Appl Genet, 2002, 104(2-3):321-328. [15] 许玉兰, 蔡年辉, 康向阳, 等. SSR-PCR反应体系建立与优化的研究概述[J].生物技术, 2012, 22(2):73-76. doi: 10.3969/j.issn.1004-311X.2012.02.048 [16] Gross-German E, Viruel M A. Molecular characterization of avocado germplasm with a new set of SSR and EST-SSR markers:genetic diversity, population structure, and identification of race-specific markers in a group of cultivated genotypes[J]. Tree Genetics & Genomes, 2013, 9(2):539-555. [17] Borrone J W, Schnell R J, Violi H A, et al. PRIMER NOTE:Seventy microsatellite markers from Persea americana Miller (avocado) expressed sequence tags[J]. Molecular Ecology Notes, 2007, 7(3):439-444. [18] Kaneko Y, Lian C, Watanabe S, et al. Development of microsatellites in Machilus thunbergii (Lauraceae), a warm-temperate coastal tree species in Japan[J]. American Journal of Botany, 2012, 99(7):e265-e267. doi: 10.3732/ajb.1100560 [19] Lavi U, Akkaya M, Bhagwat A, et al. Methodology of generation and characteristics of simple sequence repeat DNA markers in avocado (Persea americana M.)[J]. Euphytica, 1994, 80(3):171-177. doi: 10.1007/BF00039648 [20] Sharon D, Cregan P B, Mhameed S, et al. An integrated genetic linkage map of avocado[J]. Theoretical and Applied Genetics, 1997, 95(5):911-921. [21] Tsuneki S, Mori K, Kaneko S, et al. Identification and characterization of eight microsatellite loci in Machilus pseudokobu (Lauraceae), an endemic species of the Bonin Islands[J]. Conservation Genetics, 2009, 10(6):2009-2011. doi: 10.1007/s10592-009-9881-5 [22] 湛欣, 鲁好君, 赵帅, 等.红椿SSR-PCR体系建立和多态性引物筛选[J].林业科学研究, 2016, 29(4):565-570. doi: 10.3969/j.issn.1001-1498.2016.04.015 [23] 郭鑫, 倪州献, 罗建中, 等.桉树SSR-PCR体系优化及引物筛选应用[J].分子植物育种, 2017, 15(2):626-632. [24] 黄勇.基于SRAP分子标记的小果油茶遗传多样性分析[J].林业科学, 2013, 49(3):43-50. [25] Foster S A. The evolutionary process:A critical study of evolutionary theory. By verne grant[J].The Quarterly Review of Biology, 1993, 68(1):107. [26] Slatkin M. Gene flow and the geographic structure of natural populations[J]. Science, 1987, 236(4803):787-792. doi: 10.1126/science.3576198 [27] 严武平, 陈宣, 杨立荣, 等。濒危植物海南龙血树SSR-PCR反应体系优化[J].分子植物育种, 2018, 16(1):195-200. [28] Yang T T, Mu L Q, Wang J. Optimizing SSR-PCR system of Panax ginseng by orthogonal design[J]. Journal of Forestry Research, 2007, 18(1):31-34. doi: 10.1007/s11676-007-0006-z [29] 冯富娟, 赵丹, 孙晓艳, 等.红松SSR-PCR反应体系的建立与优化[J].经济林研究, 2010, 28(1):35-40. doi: 10.3969/j.issn.1003-8981.2010.01.007 [30] Zhu Q, Liao B Y, Li P, et al. Phylogeographic pattern suggests a general northeastward dispersal in the distribution of Machilus pauhoi in South China[J]. PLoS ONE, 2017, 12(9):e0184456. doi: 10.1371/journal.pone.0184456 [31] Wang B H, Zhu P, Yuan Y I, et al. Development of EST-SSR markers related to salt tolerance and their application in genetic diversity and evolution analysis in Gossypium[J]. Genet Mol Res, 2014, 13(2):3732-3746. doi: 10.4238/2014.May.13.1 [32] Xie W, Zhang X, Cai H, et al. Genetic diversity analysis and transferability of cereal EST-SSR markers to orchardgrass (Dactylis glomerta L.)[J]., Biochemical Systematics and Ecology, 2010, 38(4):740-749. doi: 10.1016/j.bse.2010.06.009 [33] Pratt T K, Stiles E W. How long Fruit-Eating birds stay in the plants where they feed:Implications for seed dispersal[J]. The American Naturalist, 1983, 122(6):797-805. doi: 10.1086/284172 [34] Gibson J P, Wheelwright N T. Mating system dynamics of Ocotea tenera (Lauraceae), a gynodioecious tropical tree[J]. American Journal of Botany, 1996, 83(7):890-894. doi: 10.1002/j.1537-2197.1996.tb12781.x [35] Chung M G, Chung M Y, Oh G S, et al. Spatial genetic structure in a Neolitsea sericea population (Lauraceae)[J]. Heredity, 2000, 85(5):490-497. doi: 10.1046/j.1365-2540.2000.00781.x [36] Martins E M, Lamont R W, Martinelli G, et al. Genetic diversity and population genetic structure in three threatened Ocotea species (Lauraceae) from Brazil's Atlantic Rainforest and implications for their conservation[J]. Conservation Genetics, 2015, 16(1):1-14. doi: 10.1007/s10592-014-0635-7 [37] Hewitt G M. Some genetic consequences of ice ages, and their role in divergence and speciation[J]. Biological Journal of the Linnean Society, 1996, 58(3):247-276. doi: 10.1111/j.1095-8312.1996.tb01434.x -



 下载:
下载: