-
竹子是我国最具价值的森林资源之一,在保障生态安全、木材安全等方面均发挥着重要作用。竹材优良的材性,是由竹子生长遗传和环境共同决定的,不同竹种及同一竹种不同产地的竹材材性存在着较大差异[1-3]。虽然竹材材性不同程度地受到不同抚育垦复措施[4]、施肥[5-6]、钩稍[7]等栽培措施的影响,但遗传差异是决定材性的主要内在因素。木质素含量是影响木材材性的重要因素,木质素生物合成涉及多种结构基因、调节基因和miRNA[8-10]。人们已经从遗传角度来研究竹子的材性特征,并开始借助分子生物学手段研究竹材材性的生物合成调控,如参与竹子木质素生物合成的基因CoCOMT[11]、PePAL1[12]、C4H[13]和PeLAC[14]等,参与纤维素合成的PeCesA1~7[15],参与木聚糖合成的PeIRX9和PeIRX10[16]等。虽然对这些基因仅是初步研究,但对认识竹子木质素的生物合成以及竹材材性的遗传调控分子机制具有重要意义。
肉桂酰辅酶A还原酶(CCR)是木质素合成的特异途径中的关键酶之一,该酶以3种羟基桂酸的辅酶A酯(香豆酰辅酶A、阿魏酰辅酶A、芥子酰辅酶A)作为底物,催化生成相应的肉桂醛,在木质素生物合成中起主导作用[17]。关于CCR基因及其编码蛋白的研究,已在拟南芥(Arabidopsis thaliana L.)、水稻(Oryza sativa L.)、小麦(Triticum aestivum L.)和玉米(Zea mays L.)等多种植物中开展[18];而对竹子CCR基因的研究仅有2例报道,即从七彩红竹(Indosasa hispida M. cv. Rainbow)克隆了IhCCR-1[19]和从巴拉圭瓜多竹(Guadua paraguayanan)中得到了GpCCR基因,并研究了GpCCR在不同组织中的表达模式[20]。然而,对于竹子CCR基因功能研究尚未得到深入开展。本研究以毛竹(Phyllostachys edulis (Carrière) J. Houz.)为研究对象,克隆PeCCR基因,利用实时定量PCR技术对其在不同组织中以及不同高度笋中的表达情况进行了分析,并利用在拟南芥异位表达的方法对其功能进行了初步研究,以期为揭示CCR基因在竹子木质素生物合成中的功能以及对竹材材性形成的影响提供理论依据。
-
本研究以毛竹为对象,分别以实生苗(0.5 a)和野外毛竹为材料,其中,前者是用购买自广西桂林的毛竹种子在实验室条件下播种培养(培养基质为腐殖土∶蛭石=6∶4,温度≈25℃,光照强度≈300 μmol·m−2·s−1)的毛竹,取不同组织样品用于基因表达组织特异性分析;后者是直接采取江西南昌(28°45'58'' N,115°45'39'' E,海拔399.0 m)野外生长的毛竹,选取不同发育阶段的竹笋(0.2、1.0、3.0、6.7 m),取笋基部(生根节的上部约1 cm处切取竹壁,约1 cm×1 cm)为样品,一部分用FAA固定液固定,用于切片观察;另一部分用液氮淬冻处理后用干冰运回实验室,存放于-80℃冰箱,用于RNA提取。
-
取上述经FAA固定液固定的毛竹笋样品,按照文献[21]方法,用聚乙二醇( PEG)将材料固定,制作切片(厚度10~15 μm),用0.05%的甲苯胺蓝O (TBO)染液染色后镜检观察,拍照记录。
-
将上述所取毛竹实生苗不同组织样品和野外毛竹笋的样品,在液氮中研磨成粉末,采用Trizol试剂,按照文献[22]方法提取各样品的总RNA,按照反转录试剂盒操作说明书(Promega公司)合成cDNA,存−20℃用于基因表达模式分析和克隆。
-
根据毛竹CCR基因(PH01001334G0240)序列设计定量引物qPeCCR-F和qPeCCR-R(表1)。以毛竹PeNTB作为内参基因[23],分别以毛竹实生苗不同组织样品和野外毛竹笋不同样品的cDNA为模板,进行PeCCR基因表达的定量分析。采用Roche Light Cycler®480 SYBR Green I Master试剂盒在耶拿公司QTower仪器上进行qRT-PCR实验,反应体系(10 μL)为:5.0 μL的2×SYBR Green I Mastermix,0.8 μL cDNA,正向引物和反向引物各0.2 μL(10 μmol·L−1),加ddH2O至反应总体积为10.0 μL。qPCR程序:95℃10 min;95℃ 10 s;60℃10 s;共40个循环。并应用2−△△Ct算法[24]分析实验结果。另外,利用前期本实验室毛竹叶、早花期花序、晚花期花序、地下茎、根、笋20 cm及笋50 cm等7个不同组织的转录组数据[25],分析PeCCR在不同组织中的表达情况。
表 1 PCR扩增所用引物
Table 1. Primers used in PCR
引物名称 Primer name 引物序列 (5′~3′) Primer sequence (5′~3′) 用途 Application qPeCCR-F TCGTCCATCGGCACAGTGTAC PeCCR定量表达分析 qPeCCR-R CCGTCTTAGCGTAGCAGTACCAG PeCCR quantitative analysis PeNTB-F TCTTGTTTGACACCGAAGAGGAG 毛竹内参基因扩增 PeNTB-R AATAGCTGTCCCTGGAGGAGTTT Amplification of internal reference gene in moso bamboo PeCCR-F ATGCCGATCGAGACAGCCGT 编码区克隆、半定量分析 PeCCR-R TCACGAGGTGATGAGATTGTCGTG Coding region cloning and semi-quantitative analysis PeCCR-F1 CGGGATCCATGCCGATCGAGACAGCCGT 表达载体构建 PeCCR-R1 GCTCTAGATTACGAGGTGATGAGAATGTCGTG Expression vector construction AtUbiquitin-F ATGGCTGAAGAGGATATCCAGC 拟南芥内参基因扩增 AtUbiquitin-R GAAACACTTCATATGGACGATGG Amplification of internal reference gene in Arabidopsis -
根据PeCCR序列(PH01001334G0240)的编码区序列和植物表达载体pC1301-35S-OCS [26]的多克隆位点,设计基因克隆引物(PeCCR-F和PeCCR-R)和添加酶切位点(BamHⅠ和XbaⅠ)的载体构建引物(PeCCR-F1和PeCCR-R1)(表1)。以毛竹笋cDNA为模板,用PeCCR-F和PeCCR-R扩增,获得编码区的片段。经测序验证正确后,以测序正确的质粒为模板用PeCCR-F1和PeCCR-R1扩增,采用BamHⅠ和XbaⅠ双酶切将PeCCR1连接到植物表达载体pC1301-35S-OCS的多克隆位点,形成植物过量表达载体。
-
将过量表达载体pC1301-35S-PeCCR-OCS质粒转入农杆菌(Agrobacterium tumefaciens Smith & Townsend)菌株GV3101中,培养并获得阳性克隆菌株。经菌液PCR验证正确后,对单克隆阳性菌株进行培养,按照蘸花法[27]转化模式植物拟南芥(Col-0),并收获种子(T0代)。用潮霉素(Hyg, 50 µg·mL−1)对T0代种子进行筛选,获得抗性植株并用PCR进行检测验证,继续用潮霉素筛选至纯合的转基因植株作为后续实验的材料。采用半定量RT-PCR方法验证在转基因拟南芥中的表达情况,同时以拟南AtUbiquitin (NM180850)为内参基因[28]。
-
播种纯合的转基因拟南芥株系,直接观察植株生长的表型变化。取生长6周的植株基部莲座叶以上2 cm的拟南芥茎,用7%琼脂固定后,进行切片制作(厚度约40 μm),经用0.05%的TBO染色后制作临时切片,观察拟南芥茎中木质素的情况。
另外,取基部莲座叶以上3 cm的拟南芥茎,用溴乙酰法测定其中木质素的含量,参照齐一生物科技(上海)有限公司的木质素含量检测试剂盒(货号:QYS-237008)说明书进行,同时以同期的野生型拟南芥作为对照。按照以下公式计算木质素含量(mg·g-1):
$ {\text{木质素}} = \frac{{(\Delta A - 0.006\;8) \times V_{\text{反总}} \times {{10}^{ - 3}} \times T}}{{0.027\;76 \times W}} $
式中:ΔA为测定管OD280值−空白管OD280值;V反总为反应总体积2.04 mL;W为样本质量;T为稀释倍数。
-
用引物PeCCR-F和PeCCR-R进行PCR扩增,产物电泳结果显示:约在1.0 kb出现1条特异条带,与预期目的基因大小一致,回收、克隆并送公司测序。测序结果表明:目的基因序列长度为1 026 bp,序列与毛竹基因组数据库中PH01001334G0240和NCBI数据库中毛竹cDNA(FP099901.1)的编码区完全一致,命名为PeCCR。该基因编码一个341 aa的蛋白,该蛋白包含肉桂酰辅酶A还原酶家族蛋白特有的保守结构域“NWYCYAK”,以及植物CCR特有的NAD(P)结合位点和识别区[17] (图1)。
-
根据毛竹转录组数据[28]中PH01001334G0240的RPKM值,分析发现:PeCCR在毛竹鞭、20 cm笋和50 cm笋中没有检测到表达,在根和叶中表达的RPKM值分别为2.380 64和1.832 46。由此表明,在不同组织中的表达存在明显差异。利用qRT-PCR方法对实验室毛竹实生苗不同组织中PeCCR的基因表达分析表明:PeCCR在各个组织中均有表达,但表达量差异明显,其中,在茎中的表达最低,根中表达量最高,其次是笋芽和叶片,在叶鞘和未展开叶中的表达量比较相近且相对较低(图2)。这与转录组数据PeCCR在根中的RPKM值最高相一致,但不同于笋中没有检测到表达。
-
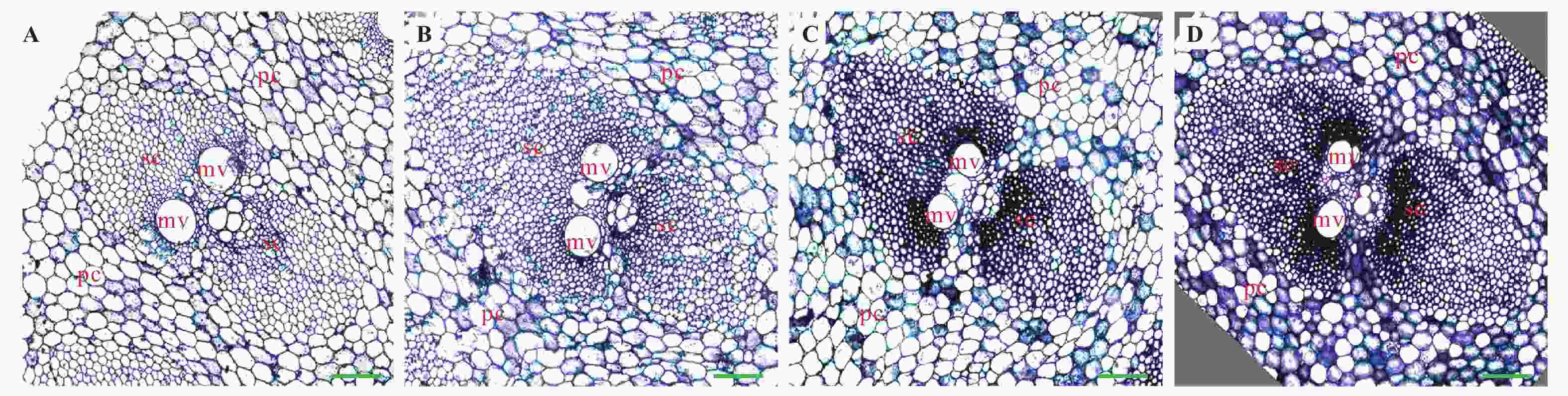
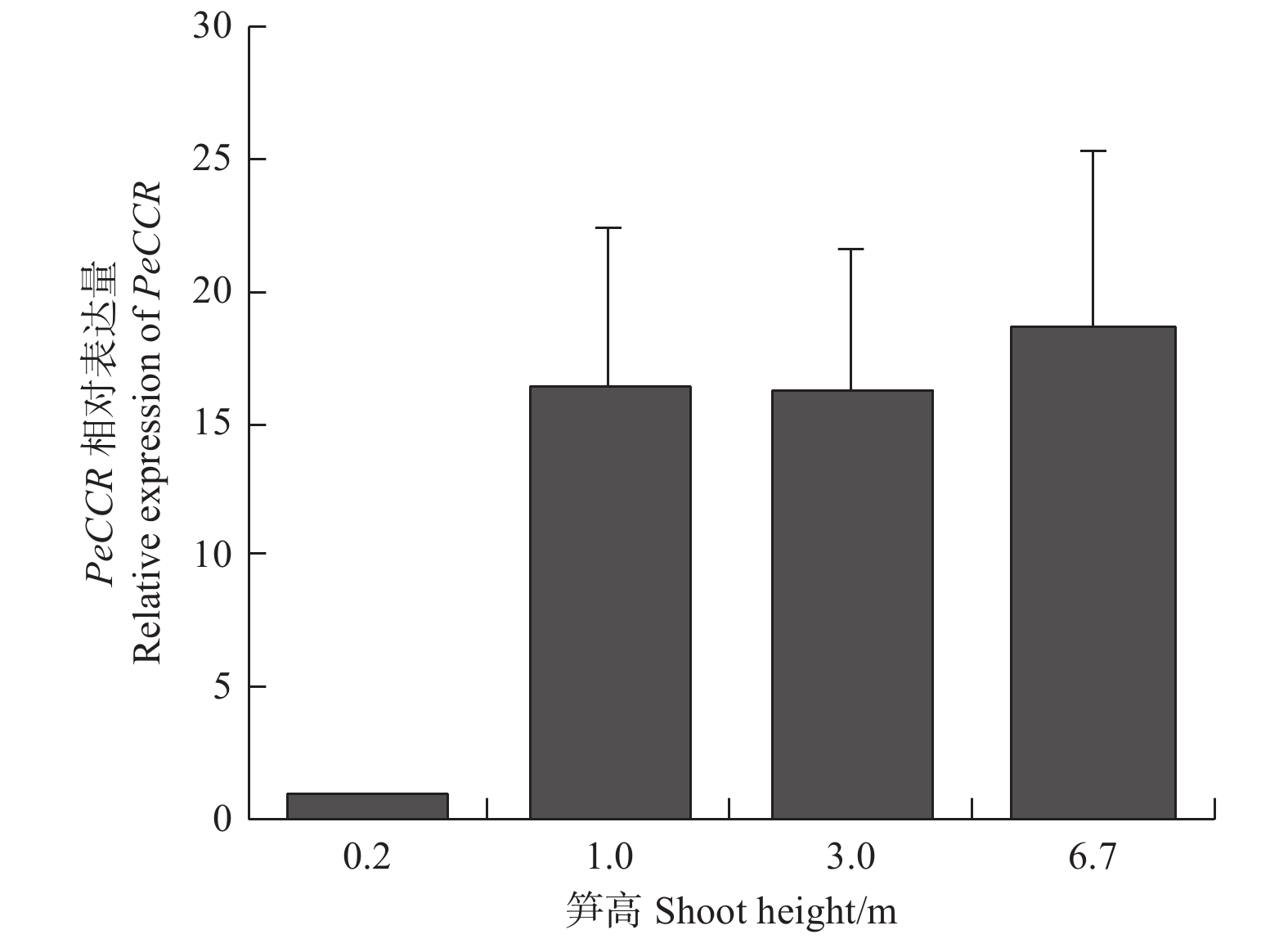
对毛竹笋样品的TBO染色镜检观察表明:随着毛竹笋高度的增加,维管束的染色加深区域明显逐渐扩大,尤其是厚壁细胞颜色明显逐渐加深,表明笋的木质化程度逐渐加强(图3)。笔者推测PeCCR的表达与竹子的木质化有关,参与木质素的生物合成,为此,对PeCCR在不同高度笋中的表达进行了定量分析。结果(图4)表明:PeCCR在0.2 m笋中的表达量相对较低,在1.0 m笋中迅速上升(约是0.2 m笋中的16倍),3.0 m笋中基本保持1.0 m笋中的水平,而6.7 m笋中PeCCR的表达量又有所上升,约是0.2 m笋中的18倍。由此表明,PeCCR基因的表达随着笋高度的增加呈上升趋势,这与竹笋的木质化程度逐渐加深相一致。
-
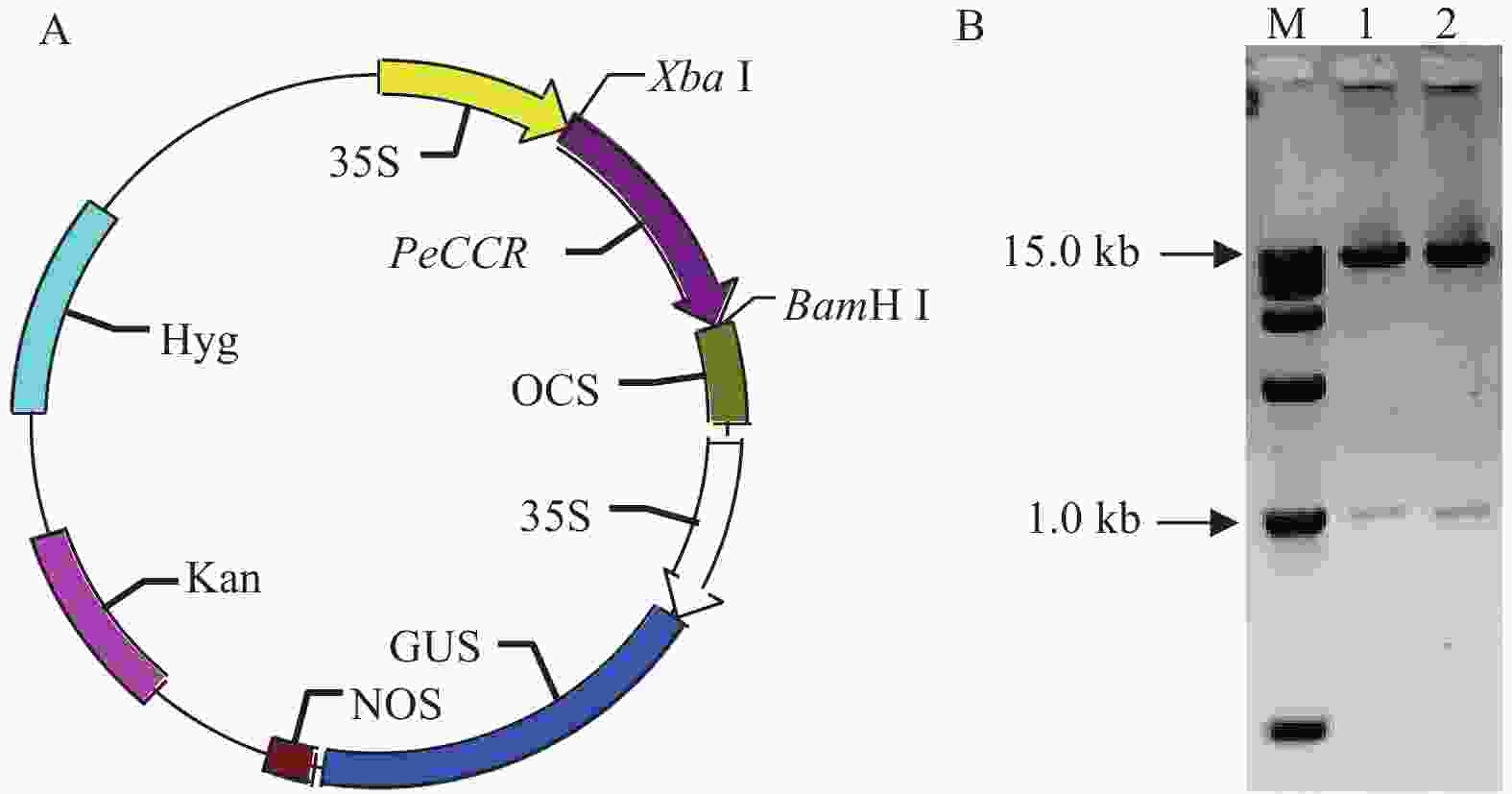
以测序正确的PeCCR质粒为模板,用PeCCR-F1和PeCCR-R1扩增的结果表明,获得了预期目的片段(图略)。回收、克隆并送公司测序表明,目的片段包含了酶切位点BamHⅠ和XbaⅠ序列及PeCCR的编码区序列。采用BamHⅠ和XbaⅠ双酶切将PeCCR连接到植物表达载体,形成过量表达载体pC1301-35S-PeCCR-OCS(图5A),质粒酶切(图5B)进一步证明获得了正确的PeCCR植物过量表达载体。
-
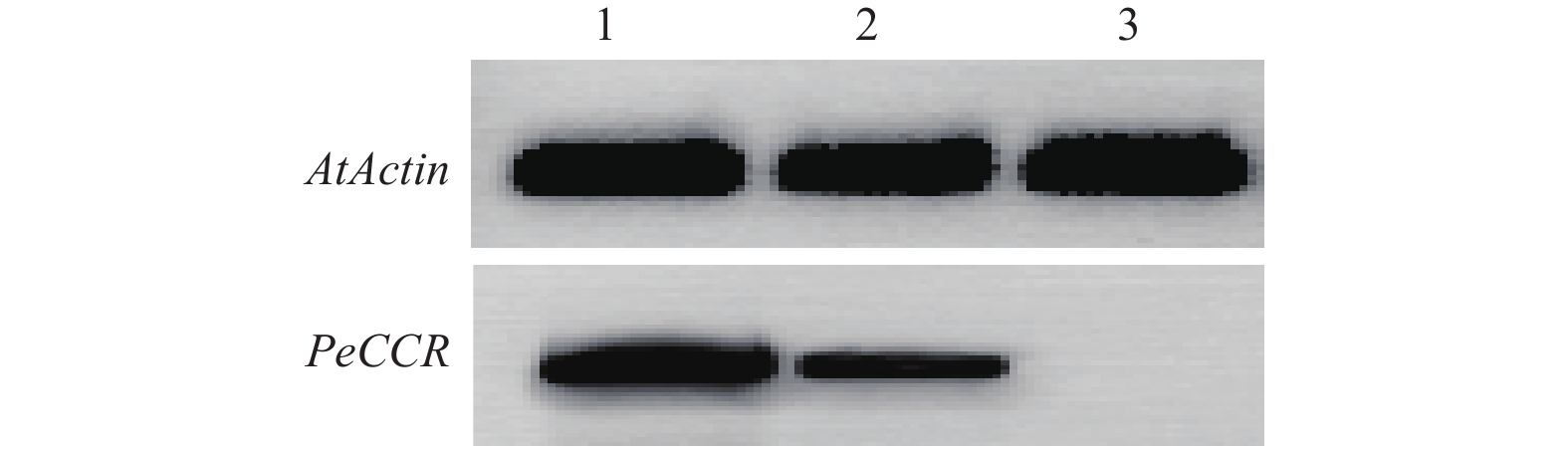
将pC1301-35S-PeCCR-OCS质粒转入农杆菌,并转化拟南芥。对获得的纯合株系表型分析发现,与野生型相比,转PeCCR基因植株叶片明显增大,且抽苔时间提前3~4 d,由此表明:过量表达PeCCR促进了转基因株系的生长发育。利用RT-PCR对获得转基因植株中PeCCR表达进行了半定量分析,电泳结果(图6)显示:在2个转基因株系中均检测到PeCCR基因表达,而野生型拟南芥中未检测到PeCCR基因表达,且2个转基因株系(Line1和Line2)中PeCCR基因的表达量不同,转基因株系Line1中的表达量高于Line2。
茎的横切组织化学染色观察显示:转PeCCR基因植株中木质部和束间纤维组织的染色面积均大于野生型(图7),说明转基因植株茎中的木质素多于野生型植株。采用乙酸-溴乙酰法对PeCCR1转基因株系木质素含量测定结果(图8)表明:2个过表达PeCCR转基因株系中的木质素含量均明显高于野生型,L1和L2分别为对照的123.1%和116.7%,且L1高于L2,这与组织化学染色法取得的结果相一致,也和2个株系中PeCCR的表达量相一致。由此表明,过表达PeCCR基因促进木质素的生物合成,木质素含量增加达到显著性水平(p<0.01)。
-
目前,木材安全已经上升到我国国家战略的高度,随着天然林保护政策的实施,木材供给不足的问题日益突出。竹材已成为木材资源的重要替代品,有效缓解了木材的供需矛盾,在我国区域经济发展和生态保护当中都发挥着不可替代的作用。研究竹材形成的分子机制,对于未来竹子的分子育种具有重要价值。毛竹基因组草图的发表与数据应用[25, 29],为从毛竹中克隆目的基因,研究其功能提供了方便。本研究克隆了木质素生物合成途径中的关键酶基因PeCCR,其编码蛋白长度(341 aa)比七彩红竹的IhCCR-1 (345 aa)和巴拉圭瓜多竹(354 aa)略短,但都含有CCR家族特有的蛋白保守结构域,是CCR家族成员之一。毛竹CCR家族包含17个成员[30],在基于毛竹、水稻和拟南芥CCR氨基酸序列构建的系统进化树中,毛竹各CCR成员均与单子叶植物水稻聚类到较近的位置,而与拟南芥的距离相对较远(图略),这与前期研究相一致[31],且PeCCR与水稻的OsCCR4 (OS09G04050)聚类在一起,二者的蛋白相似系数为88.2%,而OsCCR4是功能性CCR的候选者[32],表明PeCCR与OsCCR4可能具有相似的功能。
基于转录组数据的表达谱和实时定量PCR的结果都表明,PeCCR在毛竹根中的表达丰度最高,与小麦的Ta-CCR2(AY771357.1)在根中表达丰富[33]相类似。切片组织化学染色结果表明,毛竹笋的木质化程度随着笋高度的增加而不断加强,且其中PeCCR的基因表达量呈上升趋势,这与小麦处于木质化的根中Ta-CCR2高表达相一致[33]。研究表明,体外重组Ta-CCR2蛋白对阿魏酰CoA、5-OH-阿魏酰CoA、芥子酰CoA和咖啡酰CoA具有几乎相似的转化效率,表明它参与愈创木基木质素(guaiacyllignin, G型木质素)和紫丁香基木质素(syringyllignin, S型木质素)合成[33]。PeCCR与Ta-CCR2的氨基酸序(AAX08107.1)一致性为87.1%。在拟南芥中过量表达PeCCR,促进了转基因植株的生长发育和开花提前,显著提高其茎中木质素含量,进一步表明具有参与木质素生物合成的功能。另外,研究表明,CCR基因还能通过影响微纤夹角来影响木材材质的密度和硬度[34]。由此表明,毛竹材性形成过程中,PeCCR可能是通过参与调控木质素含量、木质素单体比例等多个方面来影响其材性的,但其在毛竹中的具体功能有待于深入研究。
-
本研究从毛竹克隆了PeCCR基因,用RT-PCT技术证明该基因在毛竹实生苗不同组织中存在表达差异;在野外随竹笋高度的增加,木质化程度加强,PeCCR基因表达量上调;在拟南芥中过量表达PeCCR,促进了转基因植株的生长发育,开花提早,木质素含量增加。本研究对于深入研究竹子木质素合成调控与竹材材性形成机制具有重要参考价值。
毛竹肉桂酰辅酶A还原酶基因PeCCR功能初步研究
Preliminary Study on the Function of Cinnamoyl-CoA Reductase Gene PeCCR of Moso Bamboo (Phyllostachys edulis)
-
摘要:
目的 为研究肉桂酰辅酶A还原酶(CCR)基因表达对竹子木质素生物合成的影响,对毛竹(Phyllostachys edulis (Carrière) J. Houz.)中PeCCR基因的表达情况进行分析,并对PeCCR基因功能进行研究,以期为利用CCR基因在竹子中开展基因工程育种提供参考依据。 方法 采用实时定量PCR(qRT-PCR)方法对PeCCR基因在毛竹不同组织以及不同高度笋中的表达进行了分析,采用RT-PCR方法克隆了PeCCR基因的编码区,构建了基因过量表达载体,采用蘸花法转化拟南芥(Arabidopsis thaliana L.),采用溴乙酰法测定转基因植株茎木质素的含量。 结果 qRT-PCR结果表明:在毛竹实生苗根中PeCCR的表达量最高,其次是笋中,而未展开叶中最低;在野外随着笋高度的增加,木质化程度加强,PeCCR基因的表达量呈上升趋势,在6.7 m笋中达到最高。克隆获得PeCCR编码区长度为1 026 bp,编码一个341 aa的蛋白,具有家族蛋白特有的保守结构域“NWYCYGK”。与野生型拟南芥相比,转PeCCR基因植株叶片明显增大,且抽苔时间提前3~4 d。茎横切的组织化学染色观察发现:转基因植株茎的木质部和束间纤维组织染色面积均大于野生型;木质素含量测定表明,2个过表达PeCCR1转基因株系中的木质素含量均明显高于野生型,分别为野生型对照的123.1%和116.7%。 结论 PeCCR基因在毛竹不同组织的表达存在差异,在笋中随高度增加其表达量上调。过量表达PeCCR促进了转基因拟南芥植株的生长发育,提高了木质素含量。 -
关键词:
- 毛竹
- / 肉桂酰辅酶A还原酶基因
- / 表达分析
- / 木质素
Abstract:Objective To reveal the effect of cinnamoyl-CoA reductase (CCR) gene expression on bamboo lignin, the expression of PeCCR in moso bamboo (Phyllostachys edulis) was analyzed, and the gene function of PeCCR was studied, which provided a reference for bamboo breeding using genetic engineering with CCR gene. Method Real-time quantitative PCR (qRT-PCR) was used to analyze the expression of PeCCR in different tissues and the shoots with different heights of moso bamboo. The coding region of PeCCR was cloned by RT-PCR and its overexpression vector was constructed. PeCCR was transformed into Arabidopsis thaliana by floral dip method, and the content of lignin in transgenic plants was determined by bromoacetyl method. Result The results of qRT-PCR showed that the expression level of PeCCR was the highest in the roots of moso bamboo seedling, followed by the shoots, and the lowest in the unexpanded leaves. Under the natural environment, with the increase of bamboo shoot height, the degree of lignification increased, and the gene expression of PeCCR showed an upward trend, reaching the highest in 6.7 m bamboo shoots. The coding region of PeCCR was 1 026 bp, encoding a 341 aa protein with a conserved domain of "KNWYCYGK" unique to the CCR family. Phenotypic analysis showed that compared with the wild type, the leaves of PeCCR transgenic Arabidopsis plants became larger obviously, and the bolting time was 3-4 days earlier. The histochemical staining of stem transverse sections showed that the staining area of xylem and inter-fiber tissue in transgenic plants were larger than that of wild type. The lignin measurement demonstrated that the lignin content of two transgenic lines overexpressing PeCCR1 was significantly higher than that of wild type (123.1% and 116.7% of the wild type control, respectively). Conclusion PeCCR was differently expressed in different tissues of moso bamboo, and it was upregulated in bamboo shoots with increasing height. Overexpression of PeCCR promoted the growth and development of transgenic Arabidopsis plants with increased lignin content. -
Key words:
- Phyllostachys edulis
- / Cinnamoyl-CoA reductase gene
- / Expression analysis
- / Lignin
-
表 1 PCR扩增所用引物
Table 1. Primers used in PCR
引物名称 Primer name 引物序列 (5′~3′) Primer sequence (5′~3′) 用途 Application qPeCCR-F TCGTCCATCGGCACAGTGTAC PeCCR定量表达分析 qPeCCR-R CCGTCTTAGCGTAGCAGTACCAG PeCCR quantitative analysis PeNTB-F TCTTGTTTGACACCGAAGAGGAG 毛竹内参基因扩增 PeNTB-R AATAGCTGTCCCTGGAGGAGTTT Amplification of internal reference gene in moso bamboo PeCCR-F ATGCCGATCGAGACAGCCGT 编码区克隆、半定量分析 PeCCR-R TCACGAGGTGATGAGATTGTCGTG Coding region cloning and semi-quantitative analysis PeCCR-F1 CGGGATCCATGCCGATCGAGACAGCCGT 表达载体构建 PeCCR-R1 GCTCTAGATTACGAGGTGATGAGAATGTCGTG Expression vector construction AtUbiquitin-F ATGGCTGAAGAGGATATCCAGC 拟南芥内参基因扩增 AtUbiquitin-R GAAACACTTCATATGGACGATGG Amplification of internal reference gene in Arabidopsis -
[1] 王昌命, 王锦王, 文久木, 等. 云南主要竹材材性与制浆造纸性能分析[J]. 中国造纸, 2008, 27(8):10-12, 22. doi: 10.3969/j.issn.0254-508X.2008.08.003 [2] Yang X Y, Fu M Y, Xie J Z, et al. Geographic variation and provenance selection for bamboo wood properties in Bambusa chungii[J]. Journal of Forestry Research, 2009, 20(3): 261-267. doi: 10.1007/s11676-009-0045-8 [3] 郭子武, 陈双林, 杨清平, 等. 牡竹属三竹种的秆形质量与材性比较[J]. 热带亚热带植物学报, 2011, 19(4):328-332. doi: 10.3969/j.issn.1005-3395.2011.04.008 [4] 曹碧凤. 不同经营措施对毛竹材用林竹材生物量的影响[J]. 安徽农学通报(上半月刊), 2011, 17(19):105-107. [5] 杨清平, 林 华, 郭子武, 等. 施肥对毛竹竹材物理力学性质的影响[J]. 中南林业科技大学学报, 2013, 33(8):28-31. [6] 周紫球, 陆媛媛, 范伟青, 等. 肥料对5年生毛竹竹材物理力学性质的影响[J]. 浙江农林大学学报, 2013, 30(5):729-733. doi: 10.11833/j.issn.2095-0756.2013.05.015 [7] 桂仁意, 邵继锋, 俞友明, 等. 钩梢对5年生毛竹竹材物理力学性质的影响[J]. 林业科学, 2011, 47(6):194-198. doi: 10.11707/j.1001-7488.20110629 [8] Lu S, Li Q, Wei H, et al. Ptr-miR397a is a negative regulator of laccase genes affecting lignin content in Populus trichocarpa[J]. Proceedings of the National Academy of Sciences of the United States of America, 2013, 110(26): 10848-10853. doi: 10.1073/pnas.1308936110 [9] Yoon J, Choi H, An G. Roles of lignin biosynthesis and regulatory genes in plant development[J]. Journal of Integrative Plant Biology, 2015, 57(11): 902-912. doi: 10.1111/jipb.12422 [10] Gui J, Luo L, Zhong Y, et al. Phosphorylation of LTF1, an MYB transcription factor in Populus, acts as a sensory switch regulating lignin biosynthesis in wood cells[J]. Molecular Plant, 2019, pii: S1674-2052(19)30173-X. [11] 李雪平, 高志民, 彭镇华, 等. 绿竹咖啡酰辅酶A-O-甲基转移酶基因的克隆与分析[J]. 分子植物育种, 2008, 6(3):587-592. doi: 10.3969/j.issn.1672-416X.2008.03.030 [12] 高志民, 彭镇华, 李雪平, 等. 毛竹苯丙氨酸解氨酶基因cDNA全长的克隆及组织表达分析[J]. 林业科学研究, 2009, 22(3):449-453. doi: 10.3321/j.issn:1001-1498.2009.03.025 [13] 金顺玉, 卢孟柱, 高 健. 毛竹木质素合成相关基因C4H的克隆及组织表达分析[J]. 林业科学研究, 2010, 23(3):319-325. [14] 李利超, 孙化雨, 娄永峰, 等. 毛竹漆酶基因PeLAC的克隆与表达分析[J]. 植物科学学报, 2017, 35(2):252-259. [15] 袁丽钗. 毛竹纤维素生物合成相关基因研究[D]. 北京: 中国林业科学研究院, 2009. [16] Zhang H, Ying Y Q, Wang J, et al. Transcriptome analysis provides insights into xylogenesis formation in Moso bamboo (Phyllostachys edulis) shoot[J]. Scientific Reports, 2018, 8(1): 3951. doi: 10.1038/s41598-018-21766-3 [17] Lacombe E, Hawkins S, Van D J, et al. Cinnamoyl-CoA reductase, the first committed enzyme of the lignin branch biosynthetic pathway: cloning, expression and phylogenetic relationships[J]. The Plant Journal, 1997, 11(3): 429-441. doi: 10.1046/j.1365-313X.1997.11030429.x [18] Barakat A, Yassin N B, Park J S, et al. Compa·rative and phylogenomic analyses of cinnamoyl-CoA reductase and cinnamoyl-CoA-reductase-like gene family in land plants[J]. Plant Science, 2011, 181(3): 249-257. doi: 10.1016/j.plantsci.2011.05.012 [19] 缪福俊, 原晓龙, 陈 剑, 等. 七彩红竹IhCCR-1基因的克隆与分析[J]. 西部林业科学, 2015, 44(5):57-61, 75. [20] 朱金鑫, 孙金金, 原晓龙, 等. 巴拉圭瓜多竹CCR基因的克隆与分析[J]. 竹子学报, 2016, 35(2):10-15. doi: 10.3969/j.issn.1000-6567.2016.02.004 [21] Yang K B, Li Y, Wang S N, et al. Genome-wide identification and expression analysis of the MYB transcription factor in moso bamboo (Phyllostachys edulis)[J]. Peer J, 2019, 11(6): e6242. [22] Gao Z M, Li X P, Li L B, et al. An effective method for total RNA isolation from bamboo[J]. Chinese Forestry Science and Technology, 2006, 5(3): 52-54. [23] Fan C, Ma J, Guo Q, et al. Selection of reference genes for quantitative real-time PCR in bamboo (Phyllostachys edulis)[J]. PLoS One, 2013, 8(2): e56573. doi: 10.1371/journal.pone.0056573 [24] Livak K J, Schmittgen T D. Analysis of relative gene expression data using real-time quantitative PCR and the 2-△△Ct method[J]. Methods, 2001, 25(4): 402-408. doi: 10.1006/meth.2001.1262 [25] Peng Z H, Lu Y, Li L B, et al. The draft genome of the fast growing non-timber forest species moso bamboo (Phyllostachys heterocycla)[J]. Nature Genetics, 2013, 45(4): 456-461. doi: 10.1038/ng.2569 [26] 孙化雨, 陈 颖, 赵韩生, 等. 毛竹β-胡萝卜素羟化酶基因的分子特征及其功能[J]. 林业科学, 2015, 51(10):53-59. [27] Clough S J, Bent A F. Floral dip: a simplified method for Agrobacterium-mediated transformation of Arabidopsis thaliana[J]. The Plant Journal, 1998, 16(6): 735-743. doi: 10.1046/j.1365-313x.1998.00343.x [28] Yang L, Lou Y, Peng Z, et al. Molecular characterization and primary functional analysis of PeMPEC, a magnesium-protoporphyrin IX monomethyl ester cyclase gene of bamboo (Phyllostachys edulis)[J]. Plant Cell Reports, 2015, 34(11): 2001-2011. doi: 10.1007/s00299-015-1846-1 [29] 赵广枝, 孙化雨, 赵韩生, 等. 毛竹基因组测序及数据应用研究现状[J]. 世界竹藤通讯, 2015, 13(3):8-12. [30] Zhao H S, Gao Z M, Wang L, et al. Chromosome-level reference genome and alternative splicing atlas of moso bamboo (Phyllostachys edulis)[J]. Gigascience, 2018, 7(10): giy115. [31] 徐 浩, 王思宁, 赵韩生, 等. 毛竹CCR基因家族成员生物信息学和表达模式分析[J]. 基因组学和应用生物学, 2019, 38(3):1168-1177. [32] Park H L, Bhoo S H, Kwon M, et al. Biochemical and expression analyses of the rice cinnamoyl-CoA reductase gene family[J]. Frontiers in Plant Science, 2017, 8: 2099. doi: 10.3389/fpls.2017.02099 [33] Ma Q H, Tian B. Biochemical characterization of a cinnamoyl-CoA reductase from wheat[J]. Biological Chemistry, 2005, 386(6): 553-560. [34] He X, Hall M B, Gallo-Meagher M, et al. Improvement of forage quality by downregulation of maize O-Methyltransferase[J]. Crop Science, 2003, 43(6): 2240-2251. doi: 10.2135/cropsci2003.2240 -




 下载:
下载: