-
麻竹(Dendrocalamus latiflorus Munro)为禾本科(Graminales)竹亚科(Bambusoideae)牡竹属(Dendrocalamus Nees)大型丛生竹种,广泛分布于我国南亚热带和热带地区,是重要的笋用竹种[1]。麻竹笋中含有大量矿物质、维生素和微量元素,是一种高蛋白、高纤维、低糖低脂的绿色保健食品[2],但麻竹笋在自然生长过程中见光会出现味苦涩、口感差、食用性下降等现象,而避光处理后麻竹笋的苦涩味物质如单宁[3]、芳香族氨基酸[4]等苦味物质含量降低,口感质量得到改善。
植物单宁属多酚类黄酮的一种,根据结构特征分为缩合单宁和水解单宁两大类,其最重要的特征是收敛性或涩性,这一性质与果蔬类产品的可食用性直接相关。植物类黄酮生物合成步骤主要包括公共苯丙烷途径、核心类黄酮-花青素途径、PA特异途径等[5-7],其中,LAR和ANR被认为是植物中单宁生物合成途径后期的关键酶[8-9]。Tanner等[10]最早在金钱草(Lysimachia christinae Hance)中克隆了LAR基因,发现其基因编码蛋白可催化产生儿茶素,证明LAR是单宁生物合成途径中一个重要的限速酶。Lepiniec等[6]发现拟南芥(Arabidopsis thaliana (L.) Heynh.)中的ANR基因编码342个氨基酸, 可将花青素还原为单宁前体之一的表儿茶素。植物中芳香族氨基酸包括苯丙氨酸、酪氨酸和色氨酸,是斑苦竹笋[11] (Pleioblastus maculatus (McClure) C. D. Chu et C. S. Chao)、绿竹笋[12] (Dendrocalamopsis oldhami Munro)呈现苦味的原因之一。芳香族氨基酸的生物合成步骤主要包括莽草酸途径和后分支酸途径[13-14],目前已在大肠杆菌(Escherichia coli (Migula) Castellani & Chalmers)[15]、葡萄(Vitis vinifera L.)[16-17]等物种作了初步的研究。如Johansson等[14]发现,野生型大肠杆菌有2个莽草酸激酶同工酶,分别由基因aroK和aroL编码,敲除aroL基因后莽草酸酶活性变得微弱,但莽草酸仍然可以积累,且自身仍可合成芳香族氨基酸。
转录组学是继基因组学后发展起来的一门学科,主要研究生物体某些特定组织或细胞在特定生长状态下基因表达产生的转录产物[18],其可作为研究物种基因功能及结构的基础和出发点[19]。近年来,转录组测序技术得到了迅速发展,已广泛应用于多个非模式生物的研究,在竹类植物中也取得了一定的进展。如王身昌等[20]利用转录组测序技术筛选得出梁山慈竹(D. farinosus (Keng et Keng f.) Chia et H. L. Fung)木质素和纤维素合成相关基因,Peng等[21]对6个不同生长高度的毛竹(Phyllostachys edulis (Carrière) J. Houz.)笋混合样品进行转录组测序,鉴定出与植物激素、细胞壁代谢相关基因,Liu等[22]利用Illumina平台对麻竹不同组织的混合材料进行转录组从头测序分析,预测得出与木质素合成相关候选基因。已有报道表明,竹类植物的转录组学研究多集中在细胞壁生物合成(木质素、纤维素等)调控方面,但针对竹笋苦涩味物质生物合成方面的研究却未见报道。本试验通过转录组高通量测序技术,对自然生长(CK)和覆土处理(EP)的麻竹笋进行差异表达基因的分析,筛选出麻竹笋中苦涩物质合成的相关基因,为麻竹笋苦涩物质合成机制的研究、相关基因的克隆以及功能分析等提供理论参考。
HTML
-
试验地位于福建省漳州市程溪镇的人工笋用林,该竹林是通过竹蔸栽植、压条埋秆等无性繁殖方式逐渐营造成林,其遗传物质来源于同一原始母竹,保证了所采竹笋基因型相同。试验设置2个处理:EP处理,对即将出土的竹笋进行堆土处理,堆土高度(50±3) cm,直径(40±3) cm;对照组(CK)为自然条件下生长的竹笋。每处理布置10个重复。竹笋生长高度至约(40±3) cm时,于秆基处截断挖取采样,每种处理选取3株无机械损伤、无病虫害的壮笋,按笋节横切分开(以竹笋基部第1个笋节为第1节),分别选取CK和EP处理第6节笋肉置于液氮中速冻,后转入-80℃冰箱保存待测。
-
按照RNeasy Plant Mini Kit(50)试剂盒(QIAGEN公司)说明书提取竹笋总RNA。用Nanodrop-2000c核酸蛋白测定仪(Thermo公司)检测RNA的纯度, 同时使用琼脂糖凝胶电泳检测RNA的质量以及完整性。
-
使用结合有poly-T寡核苷酸的磁珠从总RNA中分离出含有poly-A的mRNA,加入片段化缓冲剂(Fragmentation)将其打断成片段,以mRNA为模板,采用随机引物法合成cDNA的第1条链,加入缓冲液、RNase H、dNTP混合物、DNA聚合酶Ⅰ合成cDNA的第2条链,采用AMPure XP beads进行cDNA纯化。纯化后的cDNA经末端修复、poly(A)添加、测序接头连接及AMPure XP beads筛选得出大小合适的片段,后进行PCR扩增,建立测序文库。
-
用IlluminaTM2500测序仪对构建合格的测序文库进行双末端(Paired-end)测序,测序在浙江谷禾信息技术有限公司进行。
-
将测序得到的原始图像进行碱基读取,转换为由短核苷酸序列组成的原始数据(Raw data)。对测序结果进行测序错误率分布及GC含量分布检验,去除含有接头及低质量的序列后,获得高质量的干净序列(Clean reads)。使用Trinity软件对Clean reads进行拼接组装,所得结果进一步使用Cap3进行组装和去冗余处理获得Unigene,统计Unigene的长度和分布。
采用BLASTX软件将麻竹笋Unigene序列与NCBI non-redundant protein sequences(Nr,参数为1e-5)、Gene Ontology(GO,参数为1e-6)、Kyoto Encyclopedia of Genes and Genomes (KEGG, 参数为1e-10)、Protein family(Pfam,参数为1e-2)、Cluster of Orthologous Groups of proteins(COG,参数为1e-3)及Swiss-prot(参数为1e-5)数据库做比对注释。
-
用FPKM法(Fragments per kb per million fragments),即每100万条fragments中,对基因的每1 000个base而言,比对到该1 000个base的fragments数来衡量Unigene的表达水平[23]。用Cufflinks软件计算CK和EP处理基因表达水平的Fold-changes(P < 0.05),并用Benjamini-Hochberg方法对原有假设检验得到的显著性P值进行校正,得出FDR(False discovery rate)值[24],以log2 Fold change≥1、FDR≤0.05为筛选条件找出差异表达基因,将其注释到GO和KEGG数据库中,获得差异表达基因的功能注释及相关代谢通路信息。
-
根据前期实验结果及相关文献,在CK和EP处理转录组数据中筛选出磷酸果糖激酶(Phosphofructokinase,PFK)、烯醇化酶(enolase,ENO)、苯丙酮酸/4-羟基苯丙酮酸转氨酶(Phenylpyruvate and 4-Hydroxyphenylpyruvate aminotransferases,PPY-AT/HPP-AT)、无色花色素还原酶(Leucoanthocyanidin reductase,LAR)基因,采用Primer-BLAST在线工具进行引物设计,以甘油醛-3-磷酸脱氢酶(Glyceraldehyde-3-phosphate dehydrogenase,GAPDH)作为内参基因[25],具体引物序列见表 1。采用1.2.1的方法提取CK和EP处理竹笋总RNA,按照PrimeScriptTM RT reagent Kit with gDNA Eraser (Perfect Real Time)试剂盒说明书合成cDNA的第1条链,在Mastercycler®ep realplex荧光定量PCR仪中进行扩增反应,反应体系为20 μL。每个反应重复3次。
基因编号
Gene number基因名称
Gene name引物序列
Primer sequences退火温度
Annealing temperature/℃Unigene000373 PFK F-Primer:GTGGGAAGACAGGACTGATTAC 62 R-Primer:CCTCCTCTCAACATCCATCAAC 62 Unigene000016 ENO F-Primer:ACAACGATGGCTCACAGAAG 62 R-Primer:CTGGTCAAAGGGATCCTCAATC 62 Unigene000422 PPY-AT/HPP-AT F-Primer:CTTGACAAAGATGCCCAATCAG 62 R-Primer:CCAACACGCTCTCCATACAA 62 Unigene023521 LAR F-Primer:GGTGGAGTTCTACGATGACAAG 62 R-Primer:GATGGAGTTGCAGCAGATGTA 62 Table 1. Primer sequences
-
采用SPSS 21.0统计学分析软件分析表达差异性,通过GraphPad Prism 6.01绘图软件将所得结果绘制成柱状图。
1.1. 试验处理及样品采集
1.2. 试验方法
1.2.1. 总RNA提取
1.2.2. 测序文库制备
1.2.3. 测序
1.2.4. 测序数据处理及分析
1.2.5. 差异表达基因分析
1.2.6. Real Time-PCR
1.3. 统计分析
-
对CK和EP处理麻竹笋肉的6个样本进行转录组测序,共得到36.45 Gb原始数据,过滤掉不合格的reads后,各样本Clean reads Q30均大于85.00%,平均GC含量为53.00%(表 2)。
样品
Sample原始序列
Raw Reads
/Mb有效序列
Clean Reads
/Mb有效碱基数
Clean Base
/GbQ30值
Q30/%GC含量
GC/%CS1 46.58 41.89 6.05 88.06 53.23 CS2 37.45 33.26 4.80 86.85 53.28 CS3 43.54 39.16 5.65 88.04 52.82 ES1 43.43 38.73 5.59 87.24 51.82 ES2 41.08 36.10 5.20 85.84 53.48 ES3 35.11 31.15 4.49 86.70 53.40 注:CS1、CS2、CS3分别代表自然生长条件下竹笋的3个生物学重复(对照),ES1、ES2、ES3分别代表覆土条件下竹笋的3个生物学重复(处理),下同。
Note: CS1, CS2 and CS3 are three biological replicates of bamboo shoots of natural growth conditions(CK); ES1, ES2 and ES3 are three biological replicates of bamboo shoots covered by soil(EP); The same below.Table 2. The quality statistics of sequencing data
-
根据CK和EP 2个处理6个样品的FPKM值计算各处理间的皮尔森相关系数,结果显示:CK处理3个重复间相关系数均大于0.90,EP处理3个重复的相关系数均达0.80以上,表明各处理重复间的重复性良好(表 3)。
样本Sample CS1 CS2 CS3 ES1 ES2 ES3 CS1 - 0.98 0.98 0.89 0.79 0.77 CS2 0.98 - 0.99 0.89 0.81 0.79 CS3 0.98 0.99 - 0.90 0.84 0.58 ES1 0.89 0.89 0.90 - 0.85 0.80 ES2 0.79 0.81 0.84 0.85 - 0.81 ES3 0.77 0.79 0.78 0.80 0.81 - Table 3. The repeatability test between CK and EP experiments
-
对过滤后的数据进行拼接和去冗余处理,取每条基因中最长的转录本作Unigene,共得到53 388个Unigene序列。Unigene长度是评估转录组组装质量的重要标准之一,本实验中,长度在1 000 bp以上的Unigene有15 176个,占总数的28.43%。序列平均长度为874.16 bp,N50长度为1 484 bp(表 4),表明组装效果较为理想。
Unigene长度
Unigene length/bp数量
Number占总数比例
Percentage/%200~300 14 823 27.77 300~500 11 822 22.14 500~1 000 11 567 21.66 1 000~2 000 9 640 18.06 >2 000 5 536 10.37 总数Total number 53 388 100.00 总长度Total length/bp 46 669 712 平均长度Average length/bp 874.16 N50长度N50 length/bp 1 484 Table 4. The length statistics of Unigene distribution
-
将Unigene序列比对到Nr、GO、KEGG、Swissprot、Pfam、COG数据库中,获得Unigene的功能注释信息。最终获得注释信息的Unigene有31 462条,所占比例为58.93%(表 5), 其中,比对到Nr数据库中的Unigene最多,所占比例为58.03%,比对到同源序列比例最高的物种分别为粳稻(Oryza sativa L. subsp. japonica Kato)、短柄草(Brachypodium sylvaticum (Huds.) Beauv.)、短花稻(O. brachyantha A. Chev. et Roehr.)、粱(Setaria italica (L.) Beauv.)、节节麦(Aegilops tauschii Coss)、玉米(Zea mays L.)、籼稻(O. sativa L. subsp. indica Kato)、高粱(Sorghum bicolor (L.) Moench)、扫帚黍(Dichanthelium oligosanthes (J. A. Schultes) Gould)、大麦(Hordeum vulgare Linn.)(图 1)。比对结果表明:麻竹与稻属(Oryza L.)植物有最近的亲缘关系,占总体比例的37.08%。
数据库
DatabasesNr GO KEGG Swissprot Pfam COG 总体
Total数目
Number30 979 24 925 6 294 21 245 16 346 9 875 31 462 所占比例
Percentage/%58.03 46.69 11.79 39.79 30.62 18.50 58.93 Table 5. Unigene functional annotation statistical results
-
对CK和EP 2个处理的转录组测序结果进行比较分析,按照表达量差异倍数不小于2倍、FDR≤0.05的标准,筛选出差异表达基因1 846个,其中,在EP处理中上调表达基因有998个,占所有差异基因的54.1%;在EP处理中下调表达基因有848个,所占比例为46.9%。
-
将差异表达基因与GO数据库比较,共有701个基因得到了注释。GO分类统计显示,差异表达基因富集在生物学过程中的Unigene有171个,富集最多的是降解过程亚类,占比对到该功能类别总数的32.2%;富集在分子功能中的Unigene有530个,富集最多的亚类是酶催化活性,占比对到该功能类别总数的74.2%(表 6)。
本体Ontology GO登录号GO_accession 类目Term 基因数目Number of Unigene 生物学过程
Biological processesGO:0006091 代谢物前体和能量的产生Generation of precursormetabolites and energy 35 GO:0005975 碳水化合物代谢过程Carbohydrate metabolic process 48 GO:0009056 降解过程Cprocess 55 GO:0015979 光合作用Photosynthesis 13 GO:0065008 生物学质量调控Regulation of biological quality 20 分子功能
Molecular functionGO:0030528 转录调节因子活性Transcription regulator activity 37 GO:0003700 转录因子活性Transcription factor activity 37 GO:0005215 载体活性Transporter activity 63 GO:0003824 酶催化活性Catalytic activity 393 Table 6. GO annotation of differentially expressed genes in ma bamboo shoot
-
为了系统分析CK和EP处理所产生的差异表达基因涉及的代谢途径及行使功能,将差异基因注释到KEGG数据库中,共得到235个功能定义,显著富集的pathway有32条(FDR≤0.05),其中,注释序列最多的10条代谢通路为:抗生素生物合成,糖酵解/糖异生作用,苯丙氨酸、酪氨酸和色氨酸生物合成,光合作用碳固定,苯丙烷生物合成,丙氨酸、天冬氨酸和谷氨酸代谢,丙酮酸代谢,甲烷代谢,果糖和甘露糖代谢,甘油磷酸酯代谢(表 7)。
通路编号
Pathway ID类目
Term基因数目
Number of Unigene (所占比例)(Percentage/%)FDR值
FDRko01130 抗生素生物合成Biosynthesis of antibiotics 83(29.12) 0.00 ko00010 糖酵解/糖异生作用Glycolysis / Gluconeogenesis 31(10.88) 0.00 ko00400 苯丙氨酸、酪氨酸和色氨酸生物合成Phenylalanine, tyrosine and tryptophan 17(5.96) 0.00 ko00710 光合作用碳固定Carbon fixation in photosynthetic 14(4.91) 0.00 ko00940 苯丙烷生物合成Phenylpropanoid biosynthesis 11(3.86) 0.04 ko00250 丙氨酸、天冬氨酸和谷氨酸代谢Alanine, aspartate and glutamate metabolism 11(3.86) 0.00 ko00620 丙酮酸代谢Pyruvate metabolism 10(3.51) 0.00 ko00680 甲烷代谢Methane metabolism 9(3.16) 0.00 ko00051 果糖和甘露糖代谢Fructose and mannose metabolism 9(3.16) 0.00 ko00564 甘油磷酸酯代谢Glycerophospholipid metabolism 8(2.81) 0.02 Table 7. Significant enrichment pathway of differentially expressed genes in ma bambooshoot
-
根据Unigene在各数据库的功能释义,并结合差异基因在KEGG数据库中富集的通路,对麻竹笋苦涩味物质合成相关基因进行查找分析。结果(表 8)显示:在CK和EP处理转录组测序数据注释的结果中查找到了与苯丙氨酸、酪氨酸、单宁生物合成相关的大部分酶的基因序列,涉及到的生物代谢途径有糖酵解途径、磷酸戊糖途径、莽草酸途径和花青素途径等,其中,在糖酵解途径中,葡萄糖磷酸变位酶(Phosphoglucomutase,PGC)和果糖激酶(Fructokinase,FK)基因在CK和EP处理中的表达量无明显变化,磷酸果糖激酶(Phosphofructokinase,PFK)和烯醇化酶(Enolase,ENO)基因的表达量在EP处理中降低;糖酵解和磷酸戊糖途径所共有的磷酸己糖异构酶(Phosphohexoisomerase,PHI)、醛缩酶(Aldolase,ALDO)及磷酸丙糖异构酶(Triosephosphate isomerase,TPI)的表达量在EP处理中表现出下降趋势,而己糖激酶(Hexokinase,HK)的表达量无明显变化。在后分支酸途径中,苯丙酮酸/4-羟基苯丙酮酸转氨酶(Phenylpyruvate and 4-Hydroxyphenylpyruvate aminotransferases,HPP-AT/PPY-AT)在EP处理中表达量显著降低,分支酸变位酶(Chorismate mutase,CM)、预苯酸转氨酶(Prephenate aminotransferase,PPA-AT)、阿罗酸/预苯酸脱水酶(Arogenate/prephenate dehydratase,ADT/PDT)及阿罗酸/预苯酸脱氢酶(Arogenate/Prephenate dehydrogenase,ADH-PDH)的表达量在CK和EP处理中无明显差异。在花青素途径中,无色花色素还原酶(Leucoanthocyanidin reductase,LAR)在EP处理中表达量降低,无色花色素双加氧酶(Leucoanthocyanidin dioxygenase / anthocyanidin synthase,LDOX/ANS)和花色素还原酶(Anthocyanidin reductase,ANR)在CK和EP处理中未表现出差异表达。
代谢途径
Metabolic pathways酶基因名称
Enzyme gene name酶编号
Enzyme numberFPKM log2Fold change(EP/CK) CK EP 糖酵解途径Glycolytic pathway PGC EC:5.4.2.2 109.43 95.52 -0.20 FK EC:2.7.1.4 437.72 424.31 -0.04 PFK EC:2.7.1.11 1 061.13 434.68 -1.29* ENO EC:4.2.1.11 824.33 339.61 -1.28* 糖酵解和磷酸戊糖共有途径
The common pathway of glycolysis
and pentose phosphateHK EC:2.7.1.1 143.52 140.34 -0.03 PHI EC:5.3.1.9 177.97 112.64 -0.66 ALDO EC:4.1.2.13 1 077.43 389.82 -1.47* TPI EC:5.3.3.1 228.93 125.91 -0.86 CM EC:5.4.99.5 83.63 89.41 0.09 后分支酸途径
The posterior branch acid pathwayPPA-AT EC:2.6.1.79 42.24 40.31 -0.07 ADT/PDT EC:4.2.1.91/4.2.1.51 76.02 75.52 -0.01 ADH-PDH EC:1.3.1.78/1.3.1.12 13.24 14.22 0.11 PPY-AT/HPP-AT EC:2.6.1.5 414.91 173.23 -1.26* 花青素途径Anthocyanin pathway LAR EC:1.17.1.3 3.08 0.36 -3.10* LDOX/ANS EC:1.14.11.19 3.52 3.69 0.08 ANR EC:1.3.1.77 9.04 8.71 -0.05 注:表中“*”表示在P < 0.05水平上差异显著。Note: The“*” in the table indicates that the difference is significant at the P < 0.05 level. Table 8. Gene expression of tannin, phenylalanine and tyrosine in CK and EP experiment
-
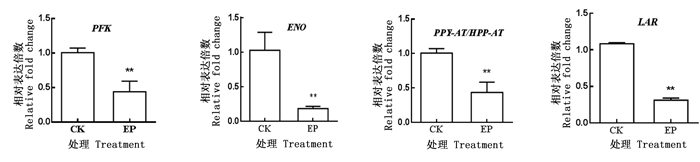
为验证转录组测序结果,本研究挑选PFK(Unigene000373)、ENO(Unigene000016)、PPY-AT/HPP-AT (Unigene000422)、LAR(Unigene023521)4个基因进行Real-time PCR实验。通过2-△△Ct 法计算各基因在CK和EP处理2个样本中的相对表达量,统计分析结果(图 2)显示:所选的4个基因在CK和EP处理中表达变化情况与测序分析结果一致,均在EP处理中呈现下调趋势,且在P < 0.01水平上差异显著。
2.1. 测序数据组装结果统计
2.1.1. 转录组测序数据统计
2.1.2. 转录组样本重复性检验
2.1.3. Unigene长度分布
2.1.4. Unigene的功能注释
2.2. 差异表达基因分析
2.2.1. 差异表达基因的筛选
2.2.2. 差异表达基因的GO功能分析
2.2.3. 差异表达基因的KEGG功能分析
2.2.4. 竹笋中单宁和芳香族氨基酸合成相关基因表达分析
2.2.5. Real Time-PCR验证
-
近年来,高通量测序技术得到了迅速发展,其通量高、成本低、灵活性高、灵敏度高的特点大大提高了测序的效率[26],为深入研究缺乏基因组数据的非模式植物的基因表达与表型之间的关系奠定了基础。高通量测序的样本可选用组织,也可选用细胞或细胞系,需根据实验目的选择样品。有研究发现,麻竹笋不同笋节的苦味物质含量差异较大,且光照对麻竹笋苦涩味物质的合成产生一定的影响[4]。前期试验结果显示,CK和EP处理第6节笋肉的单宁含量分别为1.12、0.74 mg·g-1,芳香族氨基酸的含量分别为1.31、0.94 mg·g-1,在P < 0.01水平上差异显著(数据暂未发表),且口感差异较大,因此,本试验选用了CK和EP处理的第6节笋肉作为实验材料。
本研究通过转录组测序,得到了自然生长和覆土条件下6个麻竹笋样本的36.45 Gb的原始数据,并获得了N50长度为1 484 bp的非冗余Unigene 53 388个,Unigene平均长度874.16 bp。Liu等[22]通过对麻竹不同组织材料(根、茎、叶、花、种子、笋)进行转录组测序,得到N50长度和平均长度分别为1 132、736 bp的Unigene 68 229个,本次研究测序结果与之相近。Zhang等[27]利用Illumina平台对麻竹不同发育时期花的转录组进行从头测序,获得高质量的Unigene146 395个,平均长度为461 bp;王身昌等[20]分析了梁山慈竹及其体细胞突变体的转录组测序结果,得到84 741个Unigene,其平均长度约为858 bp,N50长度为1 595 bp。总体来讲,本研究与已报道的基于高通量测序平台所得的常见竹种的转录本及Unigene的平均长度基本相似,表明此研究测序数据的拼接基本符合后续生物信息学分析。在Nr数据库中,Unigene比对到同源序列比例最高的物种为稻属植物,这与前人在与水稻、玉米和麦类作物的比较中, 竹类植物与水稻有最近的亲缘关系和更相似的基因序列特征相一致[28]。
GO富集结果表明,差异表达基因涉及到多个生物功能,其中,富集较多的有代谢物前体和能量的产生、碳水化合物代谢过程和酶催化活性,表明CK和EP处理在物质能量代谢活动上有差异。KEGG聚类分析显示,与麻竹笋苦涩味物质合成相关的多个次生代谢通路如苯丙烷生物合成、苯丙氨酸、酪氨酸和色氨酸生物合成途径在CK和EP处理中表现出显著差异,表明避光处理在转录水平上对麻竹笋苦涩味物质的合成产生了较大影响。
-
葡萄糖经糖酵解和磷酸戊糖途径分别生成磷酸烯醇式丙酮酸(PEP)和赤藓糖-4-磷酸(E4P),后经莽草酸途径、后分支酸途径生成酪氨酸、苯丙氨酸。苯丙氨酸经苯丙烷途径、类黄酮途径及花青素途径生成原花青素,即缩合单宁[29-31],其中,涉及到大量的酶,由一系列复杂的基因在时间和空间上共同作用调控,环境因素可能通过影响某些基因的表达而对苦涩味物质合成产生一定的影响。
PFK是糖酵解途径中的一个重要的限速酶,其作用是不可逆地催化果糖-6-磷酸生成果糖-1, 6-二磷酸。有研究发现,菠萝(Ananas comosus (L.) Merr.)叶片或离体的菠萝叶圆片经光照处理后,依赖于焦磷酸的焦磷酸果糖激酶(PPi-PFK)活性增高,而暗处理使酶对糖酵解方向催化活性降低[32]。本研究发现,覆土处理的麻竹笋PFK酶基因表达量降低,这可能会导致PFK酶活性降低,糖酵解代谢过程受到阻碍。ALDO催化果糖-1, 6-二磷酸可逆地裂解为甘油醛-3-磷酸和二羟丙酮磷酸,是糖酵解和磷酸戊糖途径共有代谢过程中重要的调控酶之一。目前,对于ALDO的研究多集中于激素调控和抗逆性方面。Konishi等[33]研究发现,向水稻根部外施赤霉素后,水稻根尖部位ALDO基因表达量升高。另外,有研究表明,在低温[34]、高盐[35]或干旱[36]胁迫条件下,拟南芥ALDO家族基因发生显著响应,说明ALDO基因对植物的逆境胁迫有一定的抵御作用。ENO在Mg2+的参与下,催化2-磷酸甘油酸合成PEP,是控制PEP合成的关键酶。Forsthoefel等[37]发现在高温或盐胁迫条件下,冰叶日中花(Mesembryanthemum crystallinum Linn.)的叶片和根的ENO基因有较高的转录表达水平,且叶片的ENO酶活性提高了4倍以上,表明ENO基因可能与植物的抗逆性相关。从本研究可以看出,光照下麻竹笋ENO基因的表达量是覆土条件下的2倍,说明ENO基因表达可能受光照诱导影响。
苯丙氨酸和酪氨酸的共同前体物质是由分支酸变位酶催化分支酸生成的预苯酸。从预苯酸到苯丙氨酸有两条生物合成途径,一是经PPA-AT生成阿罗酸,由ADT进一步催化阿罗酸合成(阿罗酸途径);二是经PDT生成苯丙酮酸,后经PPY-AT催化合成(苯丙酮酸途径)[29]。酪氨酸的合成与苯丙氨酸路径类似,参与的酶有PDH、HPP-AT、PPA-AT和ADH。实验结果显示,麻竹笋HPP-AT/ PPY-AT基因在黑暗条件下表达量下降,而涉及到的其它酶表达量无明显变化,表明避光处理未对阿罗酸途径产生影响,可能是通过降低苯丙酮酸转氨酶和对羟基苯丙酮酸转氨酶的活性影响苯丙氨酸和酪氨酸的合成。
LAR、ANS和ANR作为原花青素合成下游途径的3个关键酶,可以把无色花色素催化合成单宁前体物质儿茶素和表儿茶素[38]。有研究证实,LAR基因的表达和缩合单宁的合成呈正相关[39-41]。Hong等[42]发现,茶叶(Camellia sinensis (L.) O. Kuntze)经黑暗处理72 h后,ANS基因表达量降低,而LAR基因的表达量升高,茶叶内表儿茶素和儿茶素的含量变化趋势与ANS和LAR基因的表达量变化相一致。麻竹笋经过避光处理后,其单宁含量较自然生长竹笋有所下降,LAR基因表达量降低,而ANS和ANR基因的表达量保持不变,说明光照可能是通过影响LAR基因的表达而对麻竹笋单宁的合成造成影响。此外,CK和EP处理转录组测序数据也注释到了单宁、苯丙氨酸、酪氨酸合成相关酶PGC、FK、HK、PHI、TPI、CM等基因,但其表达量在CK和EP处理间未表现出差异或差异不显著,表明这些酶可能未对避光处理作出应答反应,其作用机制有待进一步研究。
3.1. 麻竹笋转录组测序分析
3.2. 麻竹笋单宁、苯丙氨酸、酪氨酸合成通路中关键基因分析
-
本研究通过转录组测序方法对覆土处理和自然生长的麻竹笋进行了差异表达基因的分析。结果显示,在避光条件下,苯丙氨酸、酪氨酸、单宁生物合成关键酶PFK、ENO、PPY-AT/HPP-AT、LAR基因表达量显著降低,可能最终影响麻竹笋苦涩味物质的合成。本研究从转录水平上初步分析了避光麻竹笋苦涩味物质合成的影响,为今后相关性状基因的克隆以及功能分析等研究提供了理论参考。






 DownLoad:
DownLoad: