-
DNA甲基化修饰是一种重要的表观遗传修饰,它通过影响DNA的构象、稳定性及其与蛋白质的相互作用方式以及染色质的结构等调控基因的表达[1],在植物生长发育以及环境响应等过程中具有重要的调节作用,并能够引起可遗传的表观变异[2-3]。植物体中DNA甲基化的建立和维持受多个基因的协同调控,这些甲基化相关基因的功能缺失和超表达均能引起基因组DNA甲基化水平的变化,从而影响基因表达;植物DNA甲基化相关基因主要有甲基转移酶(MET)基因、域重排甲基转移酶(DRM)基因、染色质重塑酶(CMT)基因和DNA甲基化转移酶2(DNMT2)基因[4]。在拟南芥(Arabidopsis thaliana)中,MET1基因主要维持CG对称位置的胞嘧啶甲基化[5-6]。拟南芥的DNA甲基转移酶MET1在配子体形成过程中通过维持精细胞中印迹基因FIS2、MPC和FWA的甲基化来实现基因的沉默[7-9]。拟南芥MET1弱突变体的表型变化不大,但其自交后代出现顶端优势减弱、植株矮小、叶形改变、营养状态差以及开花时间延迟等性状[10]。此外,MET1还在植物逆境胁迫中发挥重要的作用[6, 11-12]。Brocklehurst等[13]研究表明,在拟南芥中,超表达MET1会在编码转座因子、非编码RNA和蛋白质的基因座上随机产生新的表观等位基因,这些表观变异可传递给下一代;MET1以及其他编码表观遗传因子基因的超表达及抑制表达,提供了另一种鉴定表观遗传靶基因和创建新的表观等位基因的策略。
Zuo等[14]利用细菌阻遏物LexA的DNA结合域(DBD)和VP16的反式激活结构域开发的基于人类雌激素受体( ER)调节区域的诱导系统,称为XVE系统,它是一种高效的严格依赖于动物17-β-雌二醇诱导的嵌合式转录激活系统,能够根据雌激素的使用剂量来严格控制下游基因的表达水平。目前,XVE诱导系统能够有效控制目的基因在拟南芥[14-17]、烟草[6, 18-19]、长春花[20]、水稻[21-22]和柑橘[23]等植物中的表达,并且在拟南芥中已经通过XVE系统的应用得到了一系列的突变体[24]。目前,XVE系统已经应用于植物基因功能研究等多个方面,是比较理想的操纵基因表达和研究基因功能的化学诱导表达系统[19]。pER8-MET1载体是依据XVE系统构建,研究证明17-β-雌二醇能够有效调控烟草中外源基因的表达[6]。
本研究利用农杆菌介导法将化学诱导启动子与拟南芥甲基化转移酶基因AtMET1导入银腺杨84K(Populus alba×P. glandulosa ‘84K’)的核基因组,利用化学诱导剂17-β-雌二醇调控目的基因AtMET1的表达,研究其在杨树中的诱导表达特性,为建立杨树甲基化诱导变异体系、实现杨树品种改良和基因功能分析等奠定良好的基础。
-
植物材料为84K无菌苗。农杆菌菌株GV3101、植物表达载体pER8-AtMET1均由本实验室保存。Premix TaqTM购自TaKaRa公司(日本),引物由上海生工有限公司合成,DNA测序由Invitrogen公司(上海)完成。
-
采用电击转化法将植物表达载体pER8-AtMET1转入农杆菌GV3101,经PCR鉴定后保菌。挑取单菌落接种于2 mL LB液体培养基(含有50 mg·L−1壮观霉素和17 mg·L−1利福平)中,28℃过夜振荡培养。取2 mL菌液接种于100 mL与以上相同的LB培养液中再次振荡培养至OD值为0.6~0.8。
取继代培养4周的84K杨无菌苗顶部第3~5片叶,切成1.5 cm×1.5 cm的叶盘,垂直主脉切2~3刀。将处理好的叶片放入摇好的菌液中浸染12~15 min,将叶片置于无菌滤纸上吸净表面菌液,接种于共培养培养基(MS+0.5 mg·L−1 BA+0.05 mg·L−1NAA)上暗培养 3 d后,转至筛选培养基(MS+0.5 mg·L−1 BA+0.05 mg·L−1NAA+Timentin 200 mg·L−1+Hygromycin 3 mg·L−1)上,在温度为28℃、16 h/8 h光周期、光照强度1 500~2 000 lax下培养。当分化的芽长到1~2 cm时,将其转入生根筛选培养基(1/2MS+0.02 mg·L−1 NAA+0.05 mg·L−1 IBA+Timentin 200 mg·L−1+Hygromycin 3 mg·L−1)中进行生根筛选。
-
用植物基因组DNA提取试剂盒(TIANGEN,北京)提取转基因植株及对照叶片基因组DNA。根据已知pER8-AtMET1载体特异序列设计扩增Hygromycin基因(HPT)的引物HP,同时扩增部分HPT基因和AtMET1基因的引物HM(表1),用ABI Veriti 96孔梯度PCR仪(ABI,美国)进行PCR检测,总的反应体系为20 μL:Premix TaqTM 10 μL,Primer-F(10 μmol·L−1) 0.5 μL,Primer-R(10 μmol · L−1) 0.5 μL,DNA模板5 μL,加 ddH2O至终体积20 μL。PCR反应参数为:95℃预变性5 min;95℃变性10 s,56℃退火10 s,72℃延伸1 min 15 s,共35个循环;72℃终延伸7 min。扩增产物通过1%琼脂糖凝胶电泳检测后,用Axygen公司(美国)琼脂糖凝胶回收试剂盒回收纯化HM扩增片段,连接到克隆载体pMD™19-T Vector Cloning Kit(TaKaRa,日本),转化E. coli DH5α(TIANGEN,北京),经过蓝白斑筛选,挑取阳性克隆进行DNA序列测定。用DNAMAN 9.0软件将测序得到的基因序列与目的基因序列进行比对。
引物
名称检测
基因产物
长度/bp引物序列(5‘-3’) HP HPT 843 F: TAAATAGCTGCGCCGATGGT R: GGTTTCCACTATCGGCGAGT HM HPT-AtMET1 1 040 F: CTGTCGGGCGTACACAAATC R: ACATCAGTTTCCAGAGCCGT Table 1. The primer sequences of PCR
-
随机取1个转基因株系及未转化的84K对照无菌苗叶片(第3~5片叶子),切成1.0 cm×1.0 cm的叶盘,垂直主脉切2~3个伤口,平铺于加有100 μmol·L−1 17-β-雌二醇的不定芽分化培养基上,每个平板约放10个叶盘(叶正面朝下、保证叶盘完全接触培养基),2次重复,野生型对照处理0、12 h,转基因株系处理0、3、6、12、24、48、96、144 h。处理后随机各取5个叶盘,液氮冷冻后保存于−80℃冰箱,用于RNA提取。
-
用EASY spin Plus植物RNA快速提取试剂盒(Aidlab,北京)分别提取经雌激素诱导处理不同时间转基因株系叶片的总RNA,1 μg总RNA用于cDNA合成。首先去除残留DNA,反应体系如下:5×gDNA Eraser Buffer 2.0 μL,gDNA Eraser 1.0 μL,Total RNA 1 μg,RNase Free H2O补足至10 μL,42℃ 2 min。向上述离心管中加入体系RNase Free H2O 4 μL,5×PrimeScript Buffer 2(for Real Time) 4 μL,RT Primer Mix 1 μL,PrimeScript RT Enzyme Mix I 1 μL,混匀后37℃下反应15 min,85℃ 5 s终止反应,−20℃保存备用。将反转录产物cDNA稀释5倍作为反应模板,参照TaKaRa公司的TB GreenTM Premix Ex TaqTM II(Tli RNase HPlus)试剂盒说明配制反应体系,总反应体系为20 μL,其中,TB Green Premix TaqII(Tli RNase HPlus)10 μL,Primer-F (10 μmol·L−1) 0.8 μL,Primer-R(10 μmol·L−1) 0.8 μL,cDNA模板2 μL,用去离子水补足至20 μL。用Roche Light Cycle 480Ⅱ型荧光定量PCR仪(Roche,瑞士)进行qRT-PCR反应,反应程序为:95℃ 30 s;95 ℃ 5 s,60℃ 30 s,40 个循环;95℃ 5 s,60℃ 1 min,95℃;50℃ 30 s。引物见表2。以Actin为内参基因,每个样品6次重复,用2−ΔΔCT算法进行分析[16]。
基因 产物长度/bp 引物序列(5′-3′) Actin 195 F: AAACTGTAATGGTCCTCCCTCCG R: GCATCATCACAATCACTCTCCGA AtMET1 190 F: ACGGGTTGAGCATTGGAGTA R: ATCCCCACCAGATGACTTGG Table 2. The primer sequences of qRT-PCR
-
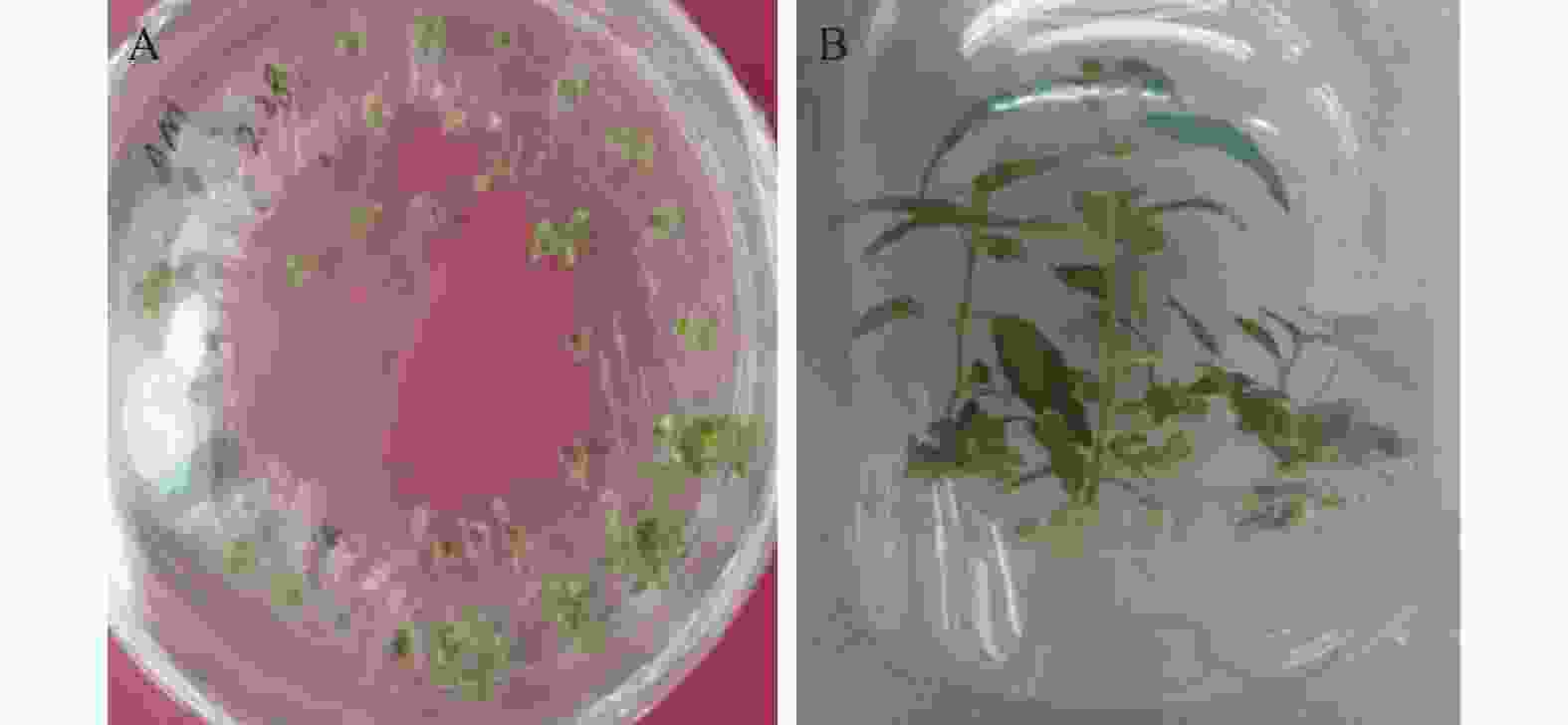
取4周大的野生型84K杨无菌苗叶片切成叶盘后进行遗传转化。经过3~4 d的共培养后将叶片放入含有3 mg·L−1潮霉素的MS分化培养基上进行抗性筛选,约10 d后叶盘切口处产生小的突起,35 d后抗性芽长至0.5 cm左右,将抗性芽连同下面的着生叶盘切下,转移到新鲜的潮霉素分化培养基上进行二次筛选分化。经过多次筛选(图1A)后,将伸长至1 cm左右的抗性芽切下,并转移到含有3 mg·L−1潮霉素的生根筛选培养基中进行生根培养,约10 d后开始生根(图1B)。总计转化叶盘数约2 700个,在分化初筛培养基上产生的抗性芽数约648个,最终获得18株潮霉素抗性植株。
-
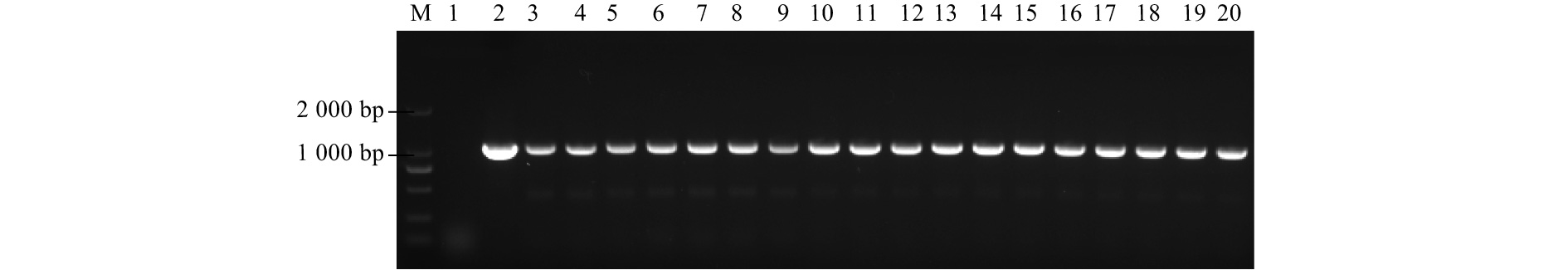
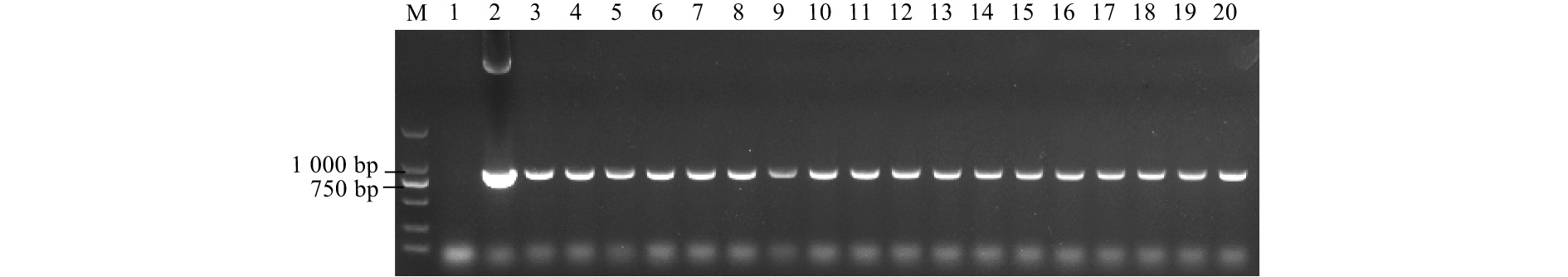
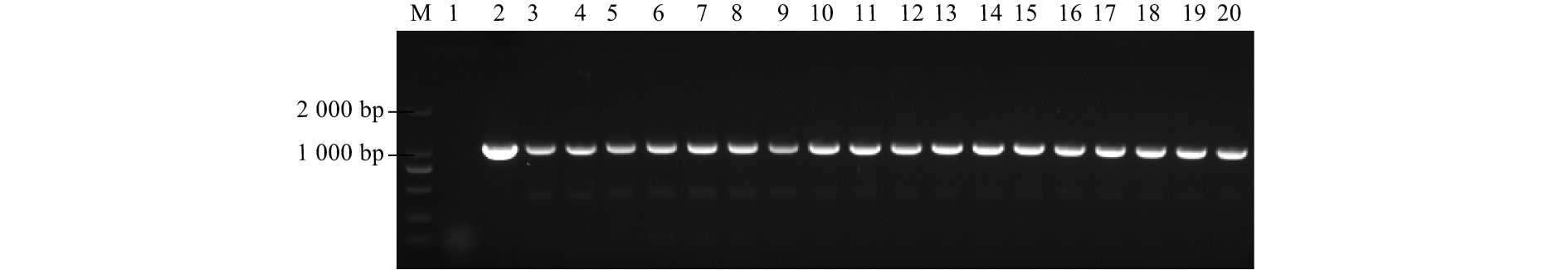
提取野生型植株和18株抗性植株的植物总DNA,以质粒为阳性对照,以野生型84K杨为阴性对照,进行PCR检测。HP引物扩增结果显示:获得的18株潮霉素抗性植株的DNA均可扩增出843 bp的目的条带,与预期目的条带大小相符(图2);为区别导入的AtMET1基因与杨树基因组内的同源基因,设计HM引物扩增从HPT基因下游的119 bp到AtMET1基因上游的233 bp的序列,包含两基因间688 bp的间隔。PCR结果显示:上述18株HP基因阳性均能扩出1条1 040 bp大小的条带,与预测目的条带大小相符(图3)。以上结果证明:诱导表达系统及目的基因已成功导入84K杨,外源基因的遗传转化效率为2.78 %。这18株阳性植株分别编号为AM-1~18#。
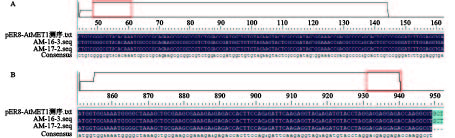
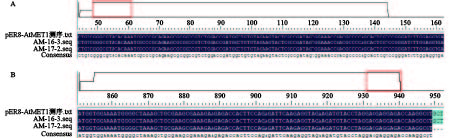
切取图3中目的条带,经过胶回收纯化后连入pMD™19-T Vector 载体(TaKaRa),挑取白色克隆进行DNA测序。测序结果表明:PCR产物序列与质粒序列比对结果相似度为100%,其中,潮霉素抗性基因的测序长度为119 bp(图4A),AtMET1基因的测序长度为102 bp(图4B)。
-
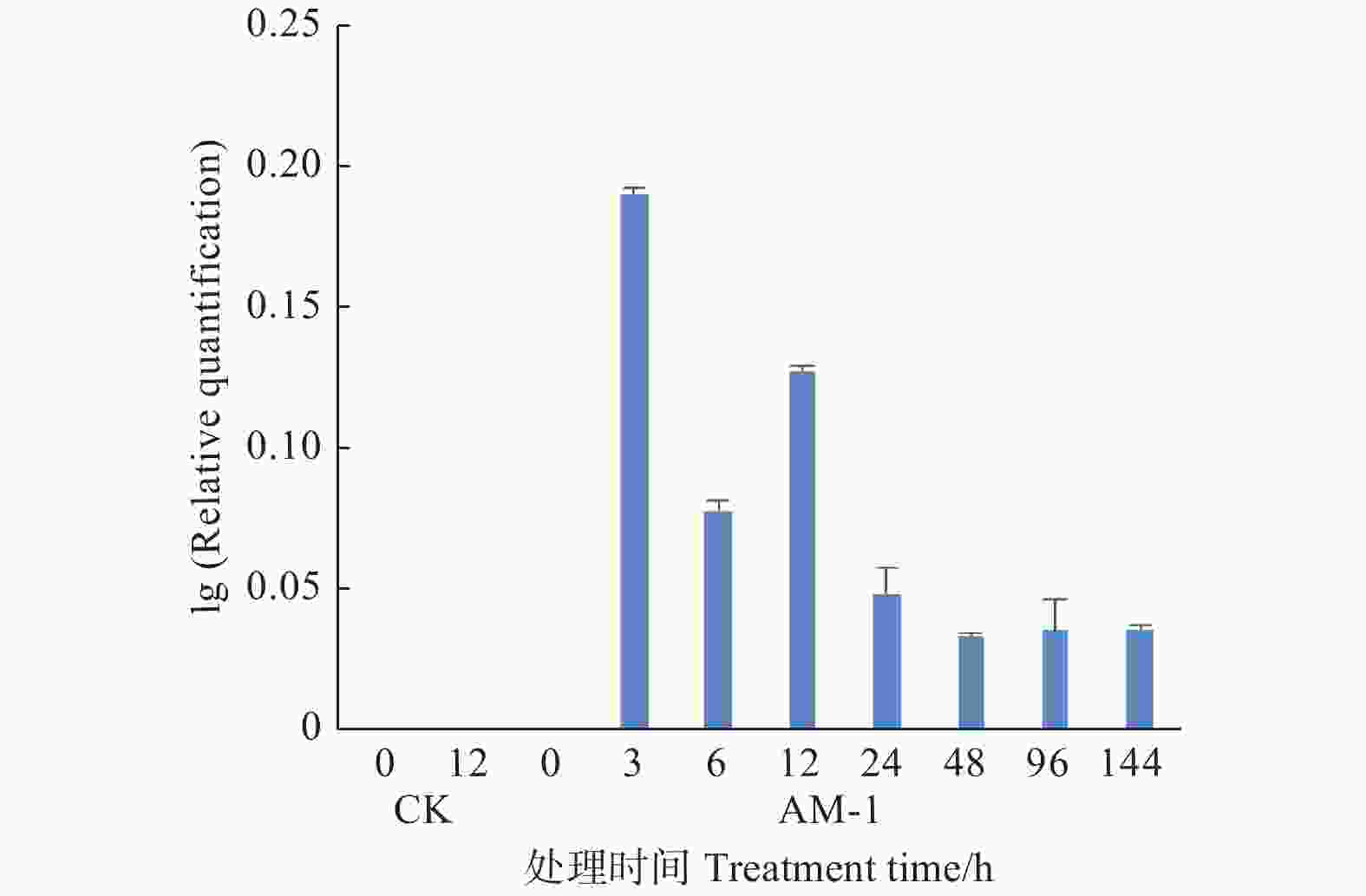
为了研究转基因杨树中XVE系统能否有效启动目的基因表达以及其表达水平随17-β-雌二醇处理时间变化的趋势,分别提取用雌激素诱导处理不同时间的AM-1#离体叶片总RNA,利用qRT-PCR检测AtMET1基因的表达情况。结果显示:用100 μmol·L−1的17-β-雌二醇处理后,野生型植株处理12 h与处理前一样,都没有目的基因的表达;转基因植株未经诱导时目的基因没有表达,诱导3 h时目的基因的表达量即达到最大值,处理6 h后表达下降,处理12 h有所回升,处理24 h以后表达量降低至不足处理12 h时的一半(图5)。以上结果说明,雌激素能够有效诱导转基因杨树中XVE系统诱导启动子的启动,使下游基因表达,且处理3 h时表达量最高,但随着处理时间的延长,诱导表达效果减弱。
-
本研究将受17-β-雌二醇诱导的化学诱导启动子及AtMET1基因用农杆菌介导法导入84K杨基因组,并利用qRT-PCR检测其中AtMET1基因的表达量随17-β-雌二醇诱导时间变化的趋势。结果表明,处理3 h目的基因的表达量即达到最大值,随后在处理6 h时表达量下降,处理12 h时有所回升,处理24 h以后表达量降低至不足处理12 h时的一半,说明化学诱导剂17-β-雌二醇能迅速有效地调控AtMET1基因在杨树中的表达。
Zuo等[14]研究显示,用2 μmol·L−1的17-β-雌二醇处理拟南芥幼苗,目的基因的表达量随着处理时间的增加而逐渐上升,在24 h时达到最高后逐渐下降;代丽娟等[19]研究显示,用2 μmol·L−1的17-β-雌二醇处理烟草幼苗,在48 h时目的基因表达量最高;梁立雄等[6]研究显示,用50 μmol·L−1的17-β-雌二醇涂抹AtMET1基因瞬时转化的烟草叶片进行诱导表达时,外源在12 h时表达量最高。本研究结果显示,转AtMET1基因杨树叶片在放置于100 μmol·L−1雌二醇培养基上时,外源基因的表达量在3 h时达到最高,这可能是三方面的原因:一是诱导剂浓度不同,本研究依据前期实验结果[6],采用100 μmol·L−1的17-β-雌二醇对转基因杨树叶片进行处理,所用的雌激素浓度是上述研究的2~50倍,可能导致诱导启动子响应时间提前;二是处理方式不同,本研究对转基因植株的离体叶片进行诱导处理,而上述研究是将雌激素加入幼苗培养基中或进行叶片涂抹的瞬时表达;三是处理对象不同,本研究首次在杨树中采用化学诱导表达的方式,不同于拟南芥、烟草等草本植物,可能由于物种的差异导致响应时间的不同。后续研究将在0~3 h之间进行时间细化处理,看其是否在3 h前就已达到平台期。在处理6 h时,目的基因的表达降低,其原因可能是AtMET1基因在杨树中表达量达到一定程度时,与RdDM(RNA-directed DNA methylation)相互作用发生了转录基因沉默(TGS,transcriptional gene silencing)[25],即siRNA(Small interfering RNA)对靶mRNA产生了降解[26]。随着诱导时间的延长,目的基因的表达量逐渐降低,这可能与17-β-雌二醇的降解有关,Snyder等[27]研究表明,当暴露于290~720 nm之间的模拟太阳光时,光降解17-β-雌二醇可达26%。
本研究发现,XVE系统在杨树中对目的基因AtMET1的调控强度低于其在烟草中对目的基因的调控强度[6],其原因可能是其表达方式上的差异导致的,在烟草中所采用的是瞬时表达方式,而本实验中所采用的是稳定表达方式[28]。此外,本研究通过遗传转化,获得了潮霉素抗性芽648个,经生根筛选及分子检测最后获得了18株转基因植株,遗传转化效率仅为2.78%,低于以往84K杨的遗传转化效率7%[29]。因为前期实验已经确定了最佳的潮霉素分化选择压[4],假阳性较高不可能是由于分化培养基中潮霉素选择压偏低导致的。其原因主要是由于叶盘筛选培养时边缘上翘导致部分非抗性再生芽的产生,以及转化过程中出现了嵌合体[30]。
本研究将受17-β-雌二醇调控的XVE系统及AtMET1基因成功导入白杨派优良品种84K杨的基因组,通过qRT-PCR证实AtMET1基因能够在化学诱导剂的诱导下表达,并且随诱导时间的不同而表达量有很大差异。由于植物不具有类似的激素系统[31],植物生长环境下外源基因并不表达,不会影响植物的正常生长发育。通过人为17-β-雌二醇处理,能够严格控制外源基因AtMET1的表达,进而能够通过对转基因植株诱导前后基因组甲基化状况以及表型性状的对比,排除转基因过程中其他因素干扰所导致的突变[19],为进一步研究MET1基因在杨树基因组甲基化调控方面的作用机制奠定基础。
-
本研究在前期研究[6]的基础上,将含有AtMET1基因的载体转化农杆菌感受态细胞,通过叶盘法侵染、潮霉素筛选,获得阳性植株;通过 PCR扩增及DNA测序,结果表明,化学诱导启动子及目的基因已成功导入84K杨基因组中,获得了84K杨的转AtMET1基因植株18株;同时,通过化学诱导表达实验,证明了化学诱导启动子在杨树中能够有效发挥作用,并且目的基因的表达受到17-β-雌二醇的严格控制,最适雌激素处理时间是3 h,但随着时间的延长效果减弱。为杨树品种改良以及基因功能分析等奠定了良好的基础。
Genetic Transformation of AtMET1 in Populus alba × P. glandulosa ‘84K’ and Its Chemical-inducible Expression Analysis
- Received Date: 2019-01-23
- Accepted Date: 2019-04-22
- Available Online: 2020-05-01
Abstract:




 DownLoad:
DownLoad: